Induced Fit Dcoking
1. 前言
蛋白-配体的结合构象,最初提出了锁钥模型,即认为蛋白质和配体在结合前后各自构象不变化,如钥匙和锁一样配对结合;但在实际生化过程中,配体结合口袋时产生的分子间作用力会诱导彼此产生构象变化,这被称为诱导契合(Induced Fit)效应,同时还需要考虑水在蛋白、配体结合中的影响。
Hermite平台的Induced Fit Dcoking模块通过模拟药物分子与靶点结合时产生的“诱导契合”效应,精确预测药物与靶点的结合模式。
2. 使用方法
2.1 入口
- 左侧通用菜单栏Menu → Function → Virtual Screening → Induced Fit Docking
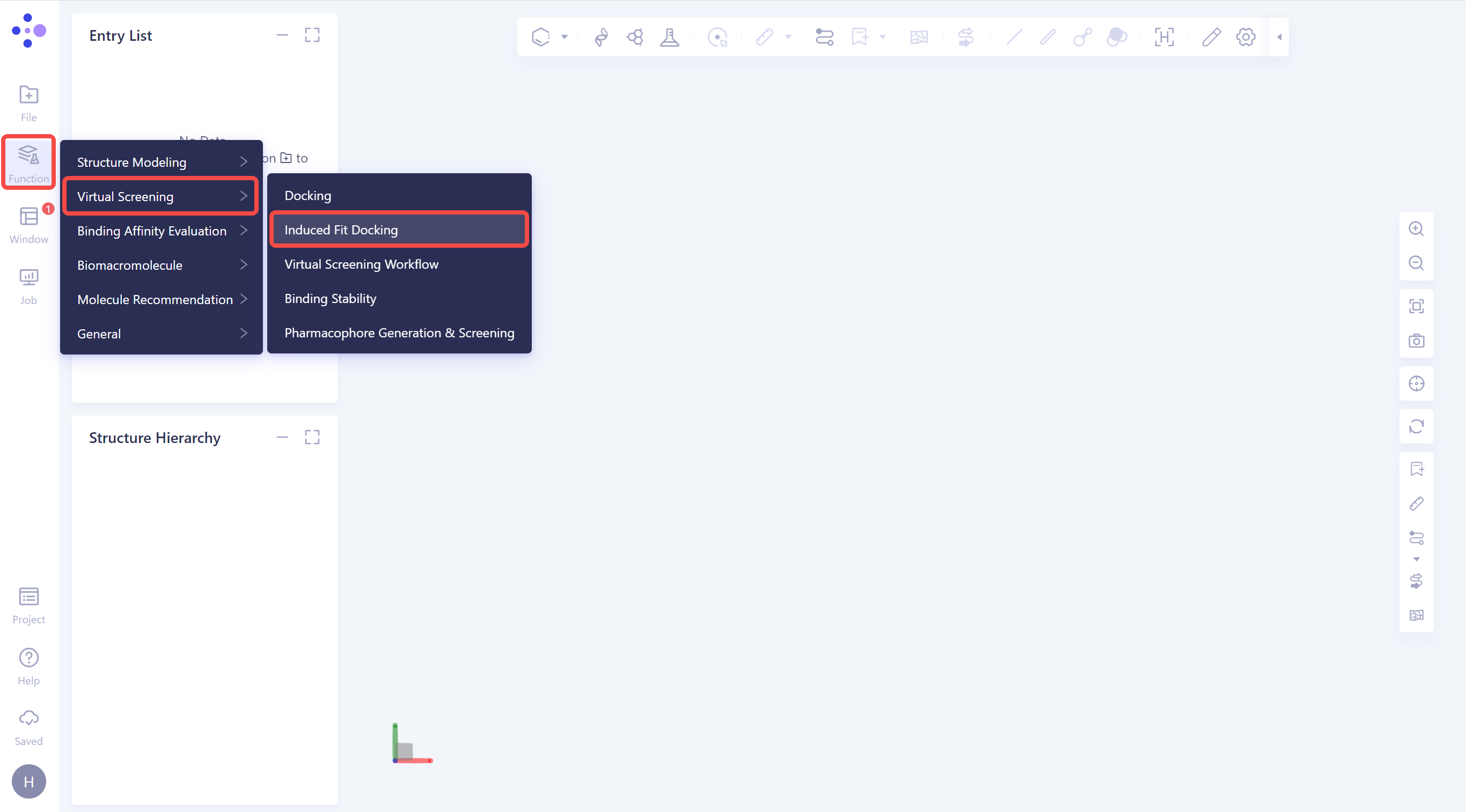
- 右侧出现Induced Fit Docking的操作框(红框内所示),整体界面如下:
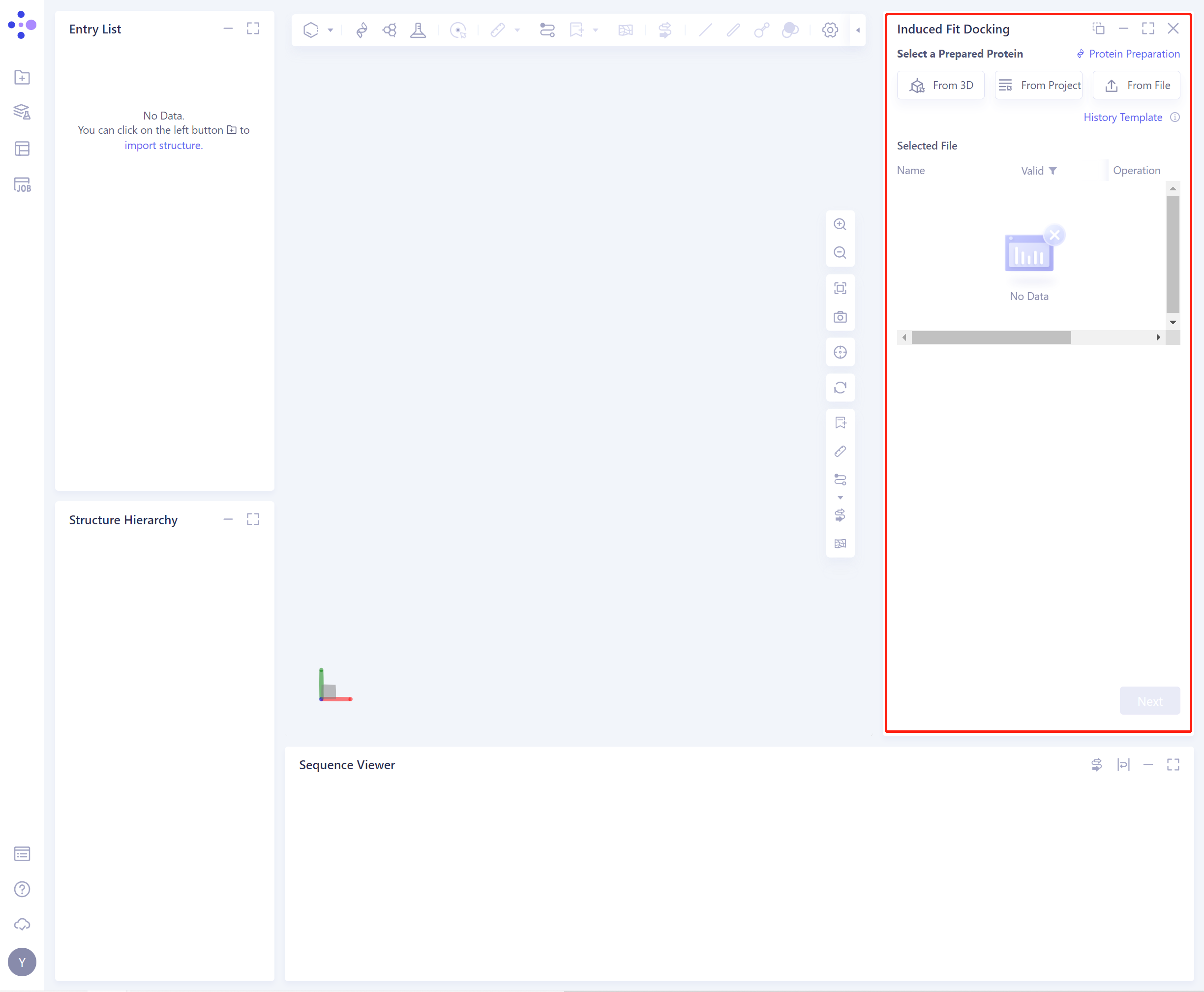
2.2 操作
-
导入蛋白结构有3种方式:
-
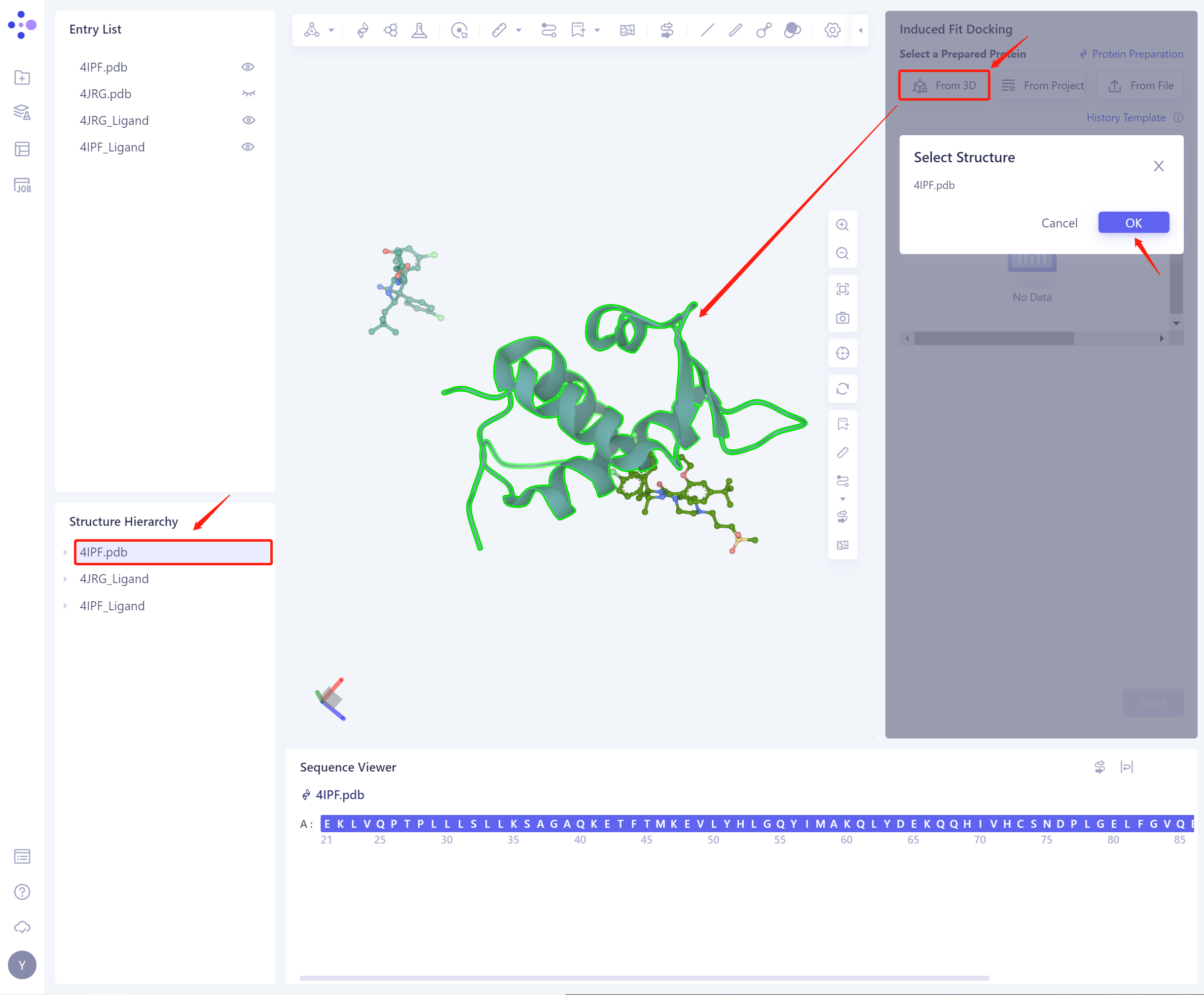
1)From 3D Workspace:从图形化组件中选择蛋白。3D Workspace中只支持蛋白级别的选择,可以在Hierarchy中选择(联动3D)。
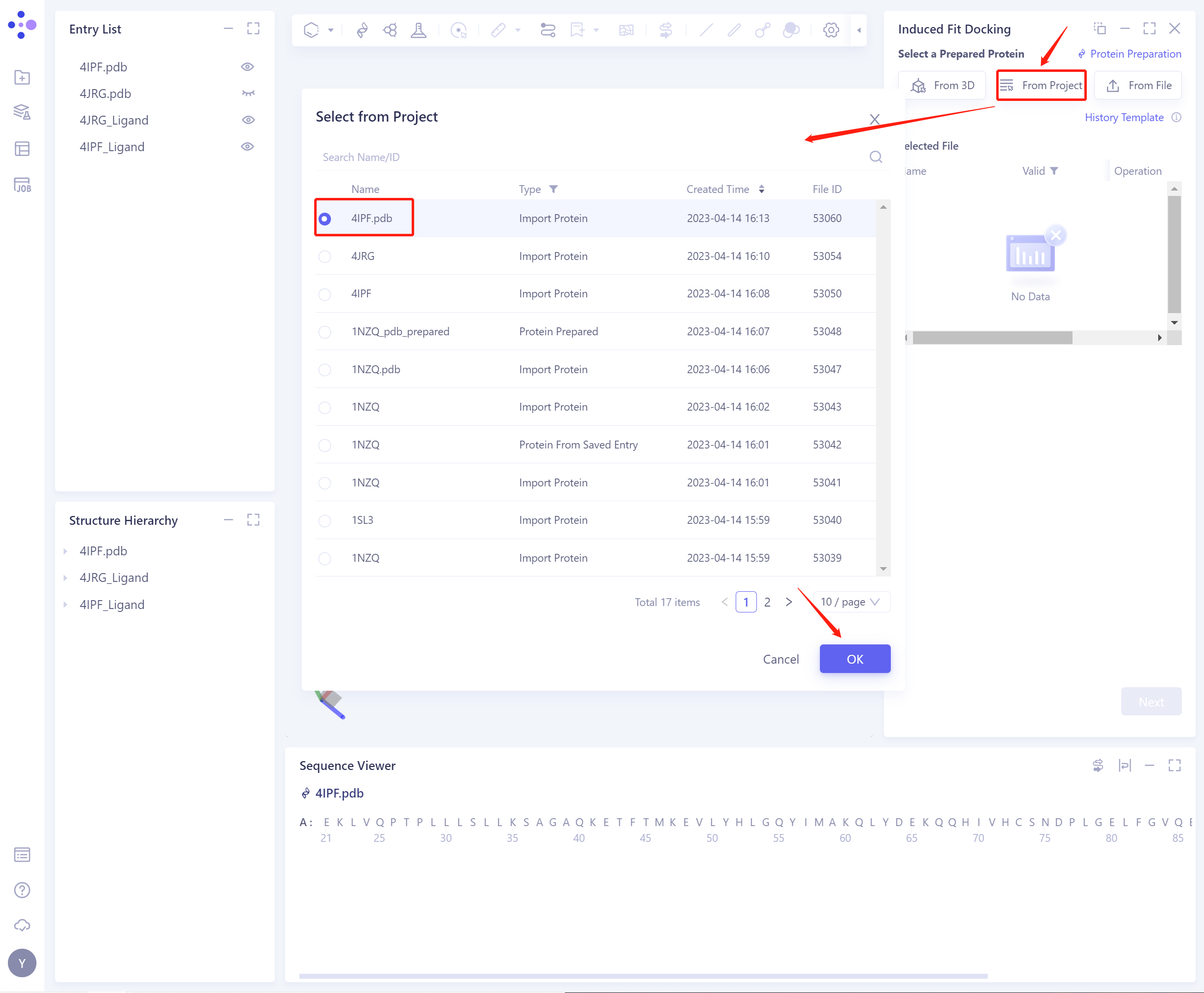
- 2)From Project:从历史项目中选择蛋白。
- 在弹出的Select from Project操作界面中,可通过 Search Name/ID 按文件名称和ID搜索文件,支持调整类型(Type)选择蛋白文件。
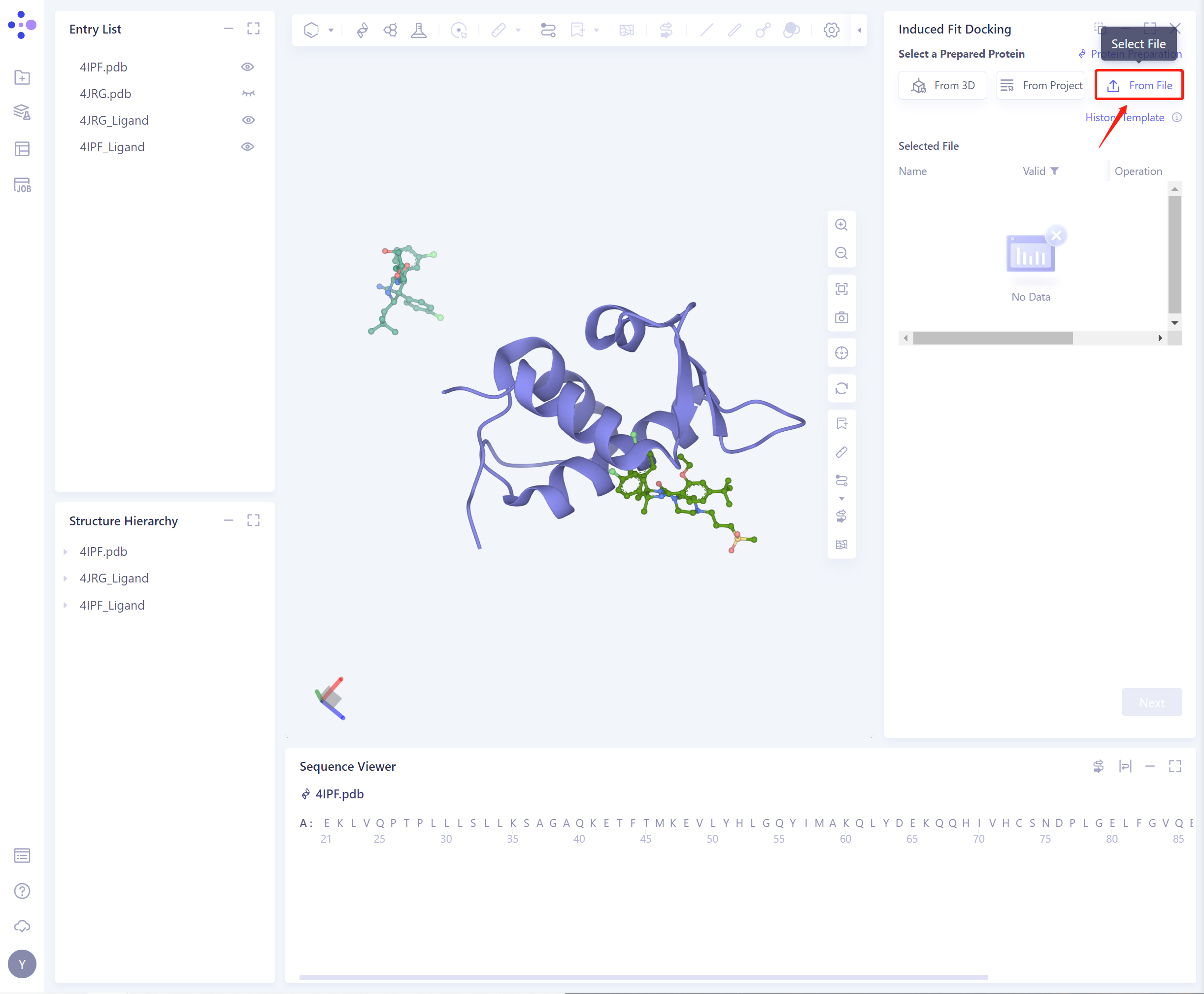
- 3)From File:上传本地蛋白文件,支持.pdb格式。
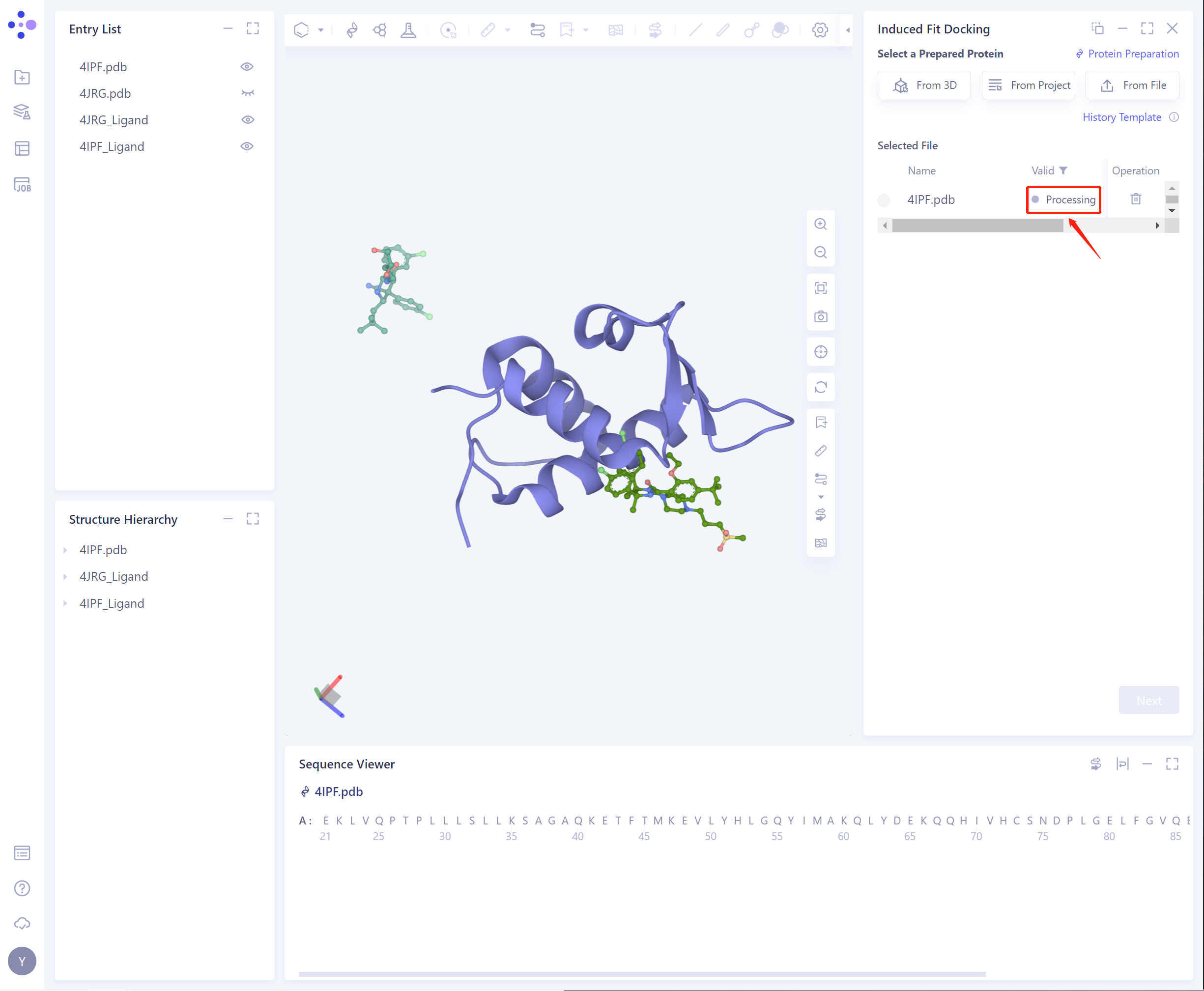
- 选择后的蛋白会被检查力场,下图为检查中。
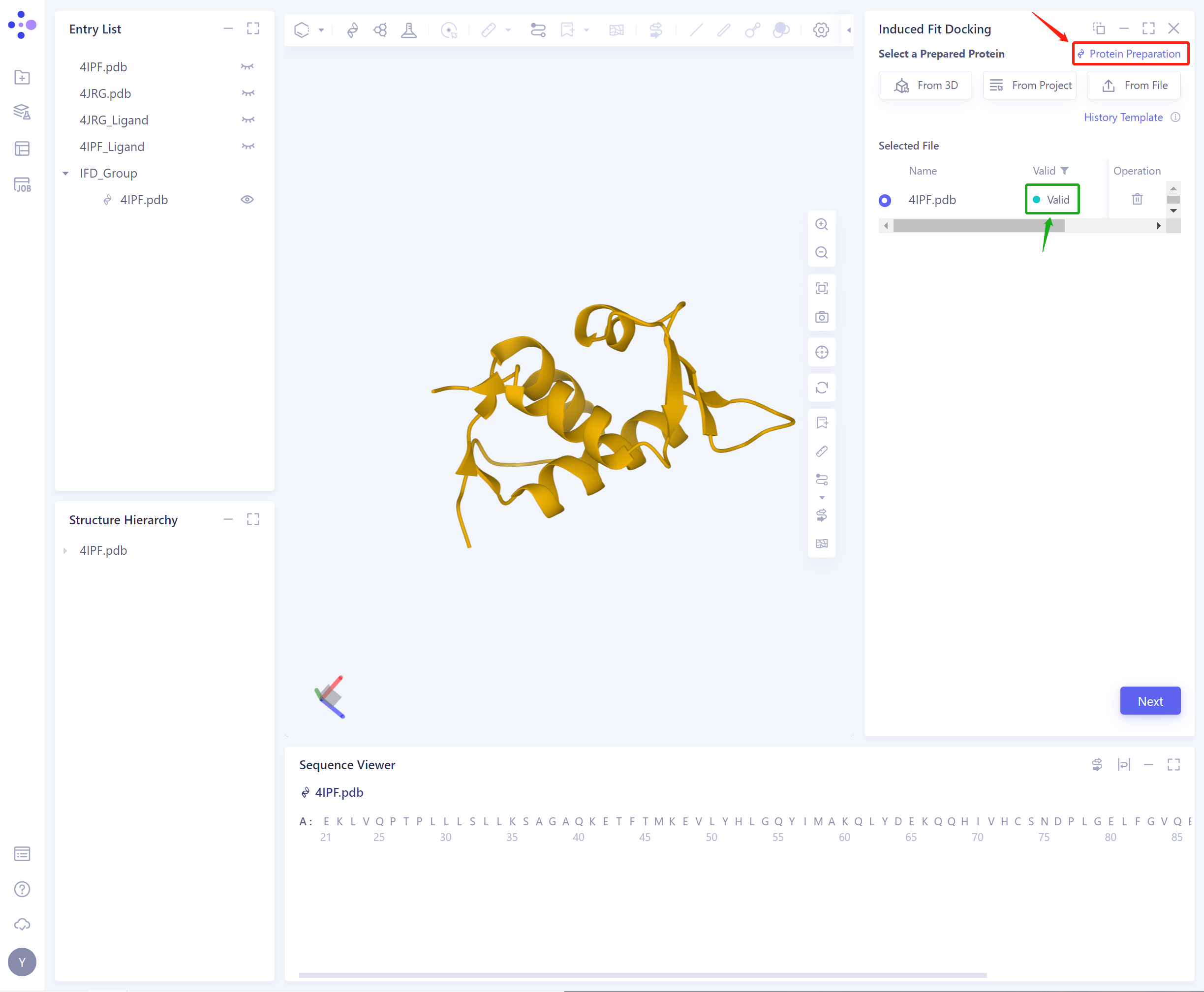
- 若蛋白力场检查不通过(此处为Valid,即力场检查通过),需要进行蛋白准备(Protein Preparation,快捷入口见图中右上红框)。
-
蛋白力场检查通过后,可继续使用功能。
-
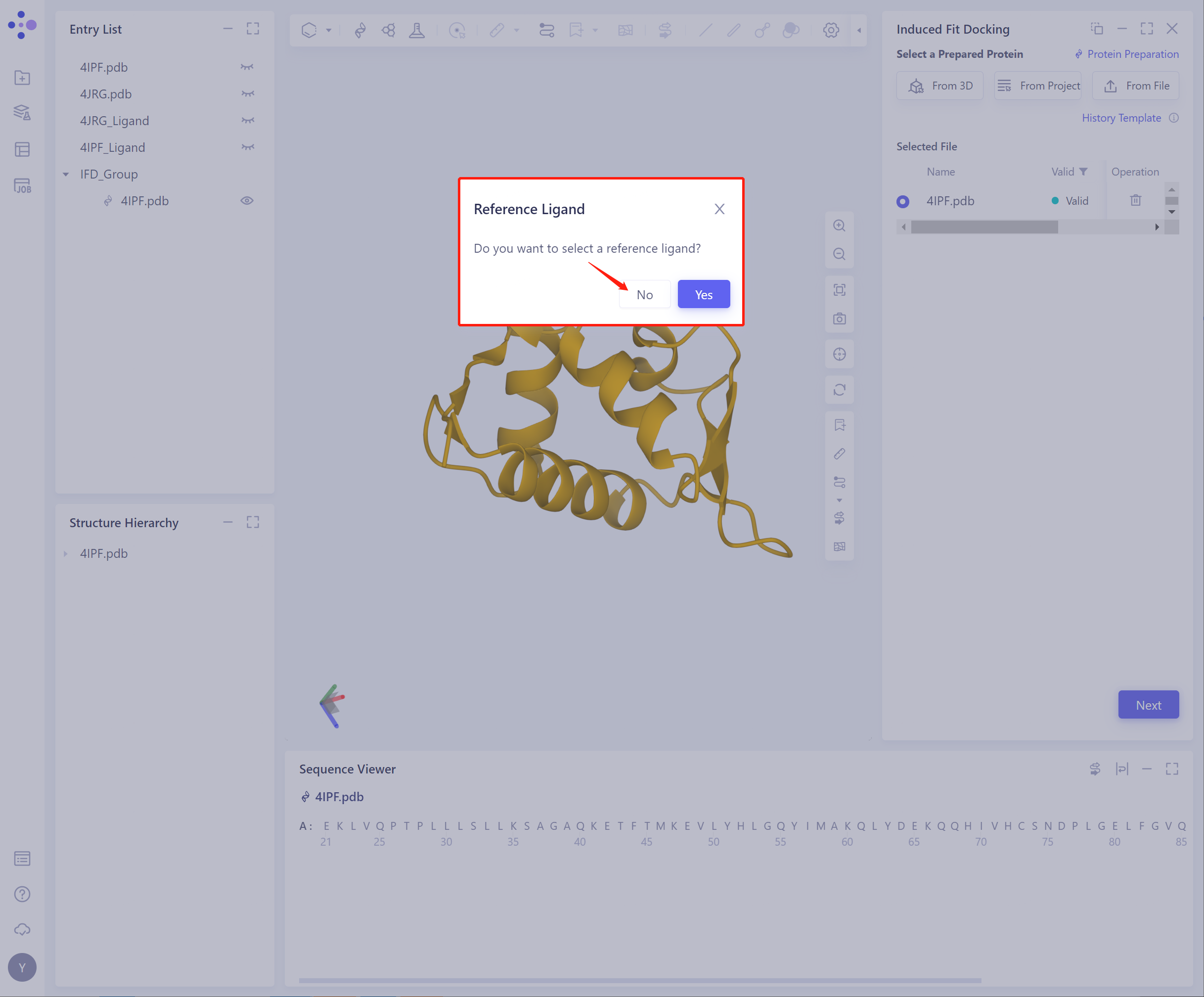
点击Next,提示是否选择reference ligand:
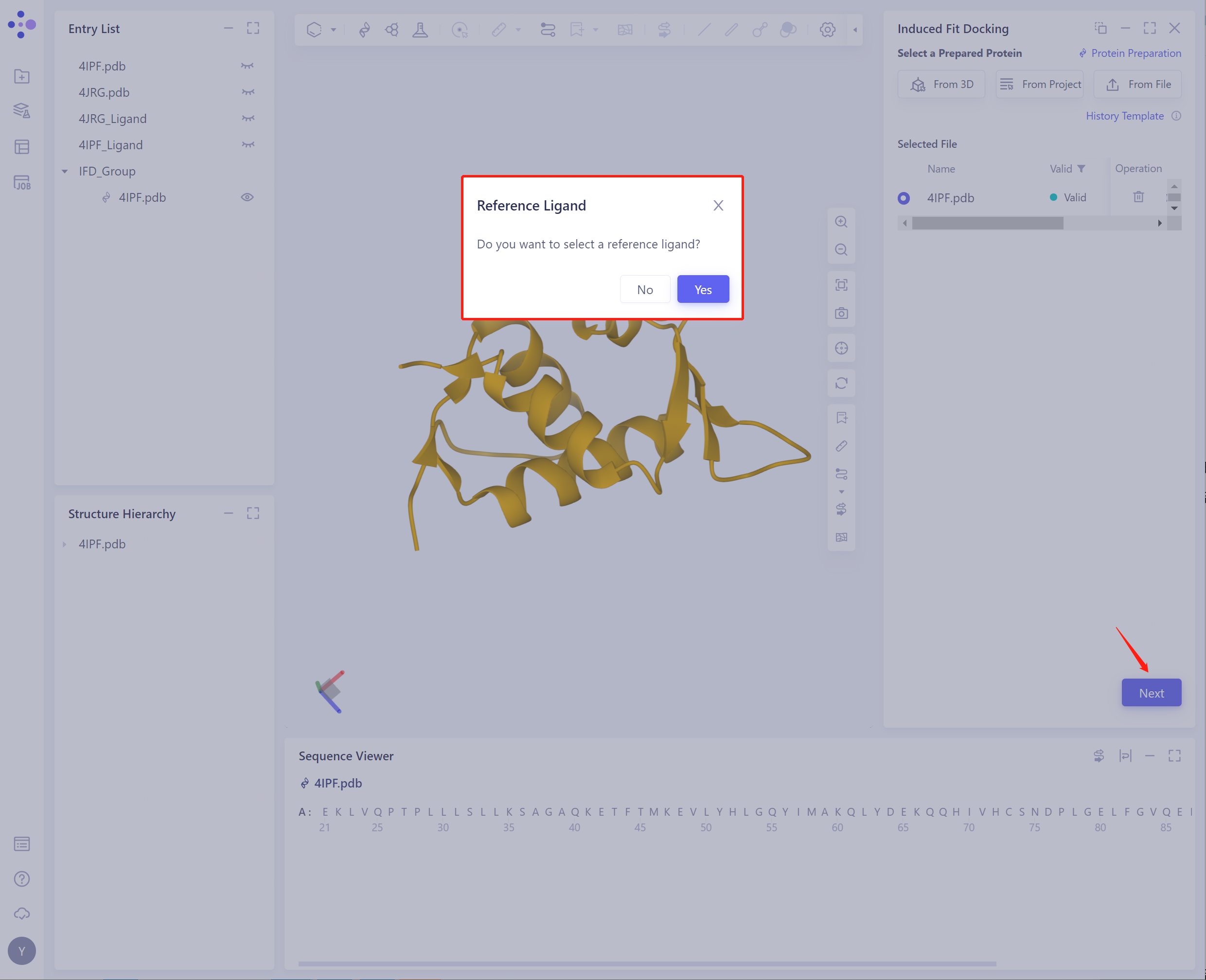
-
路径一:是否选择Reference Ligand: 点击Yes,Select a Reference Ligand
-
导入ligand有3种方式:
1)From 3D Workspace:从图形化组件中选择配体。3D Workspace中只支持Residue级别的选择,可以在Hierarchy中选择(联动3D)。
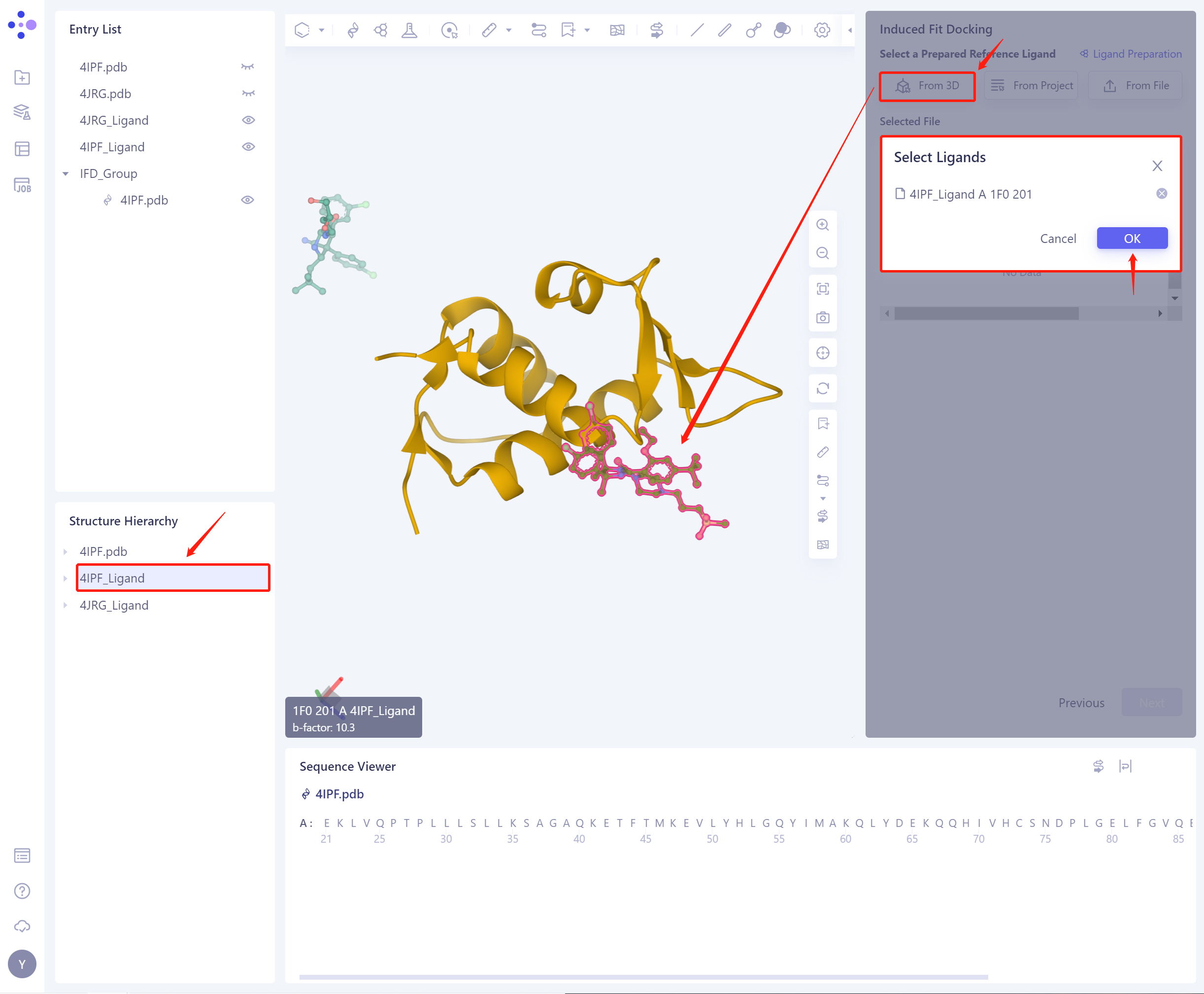
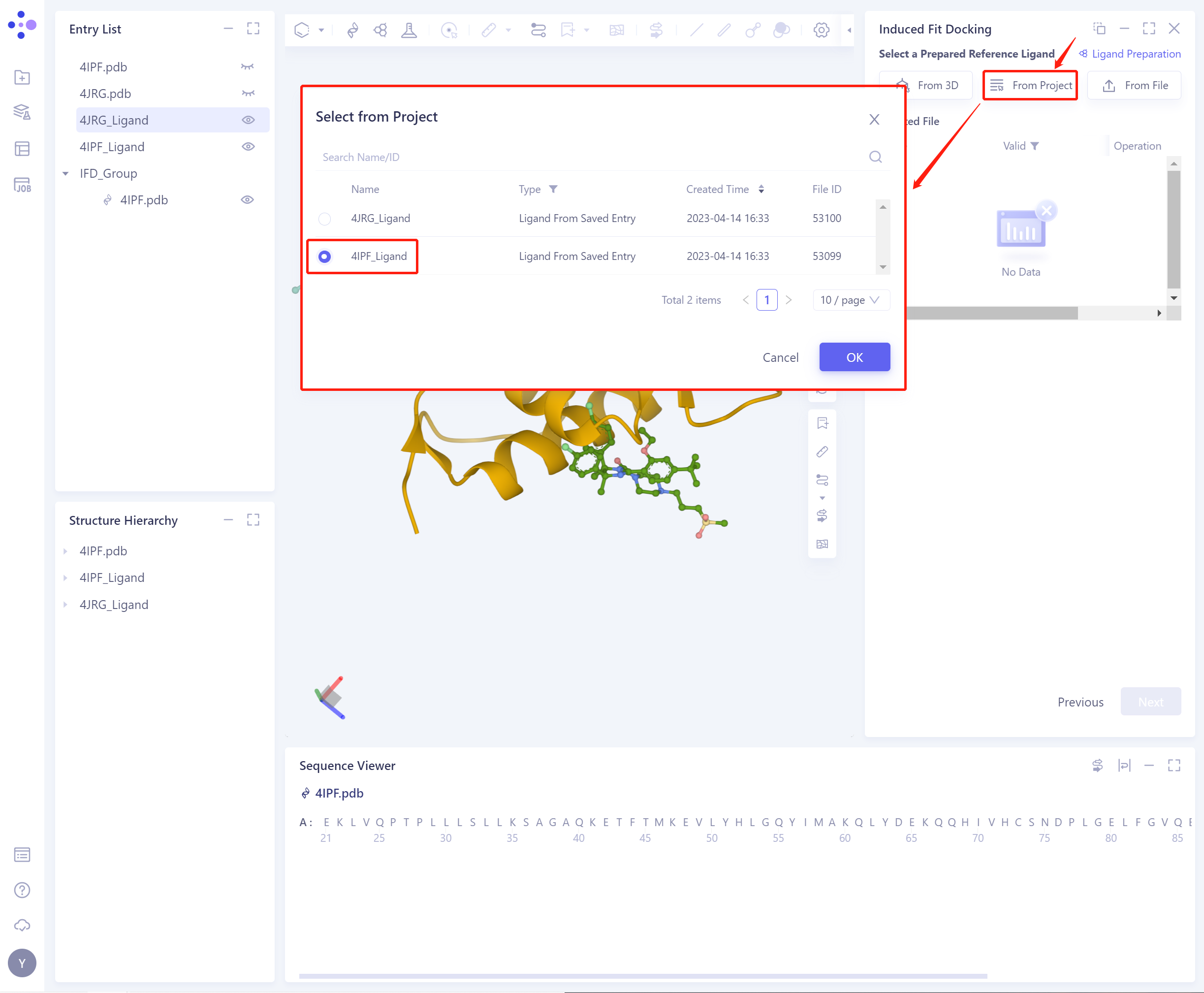
2)From Project:从历史项目中选择配体。
- 在弹出的Select from Project操作界面中,可通过 Search Name/ID 按文件名称和ID搜索文件,支持调整类型(Type)选择配体文件。
3)From File:上传本地配体文件,支持.sdf/.mol格式。
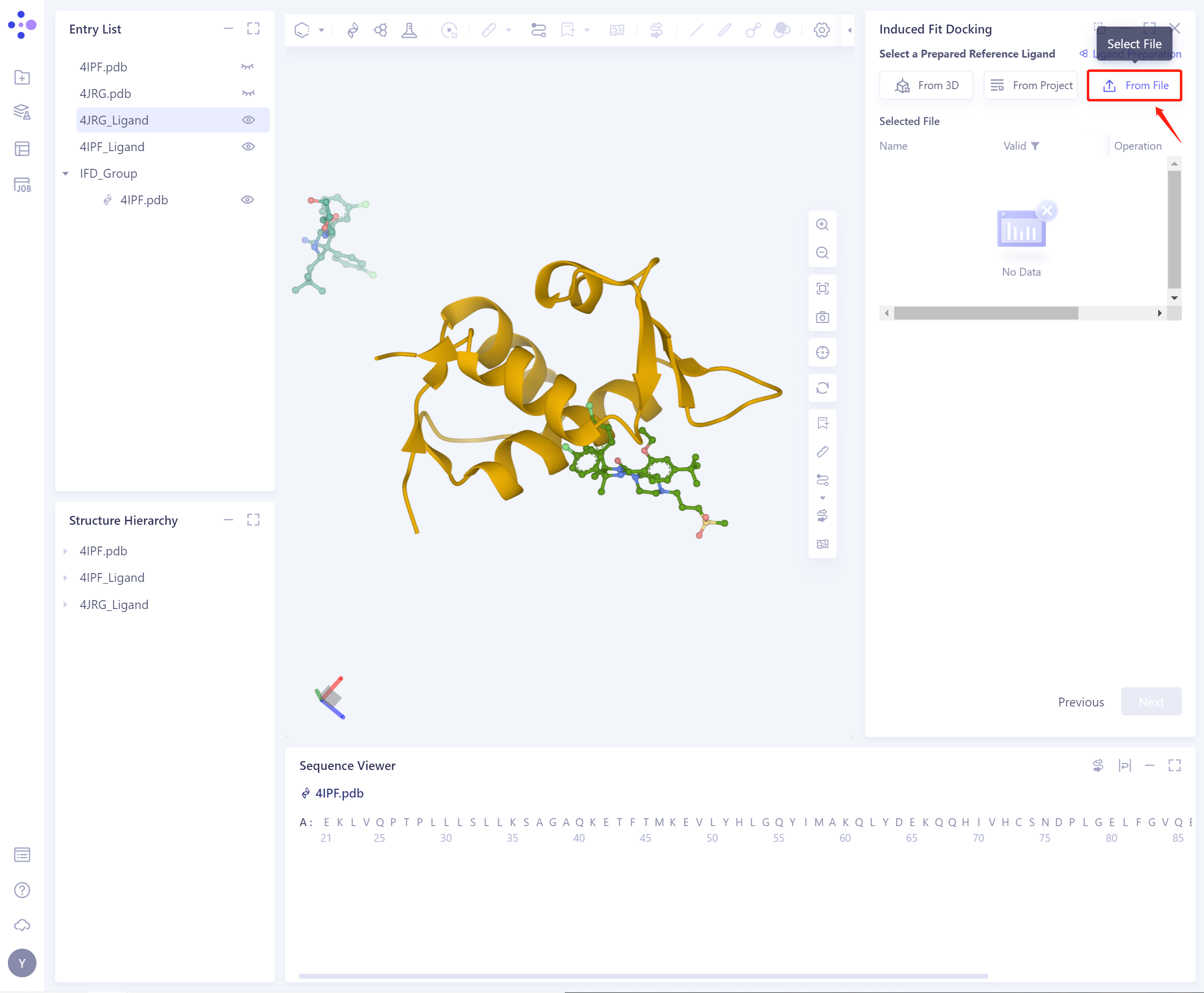
- 导入配体前,需要选择是否修复配体可能丢失的bond信息,默认选择Yes。
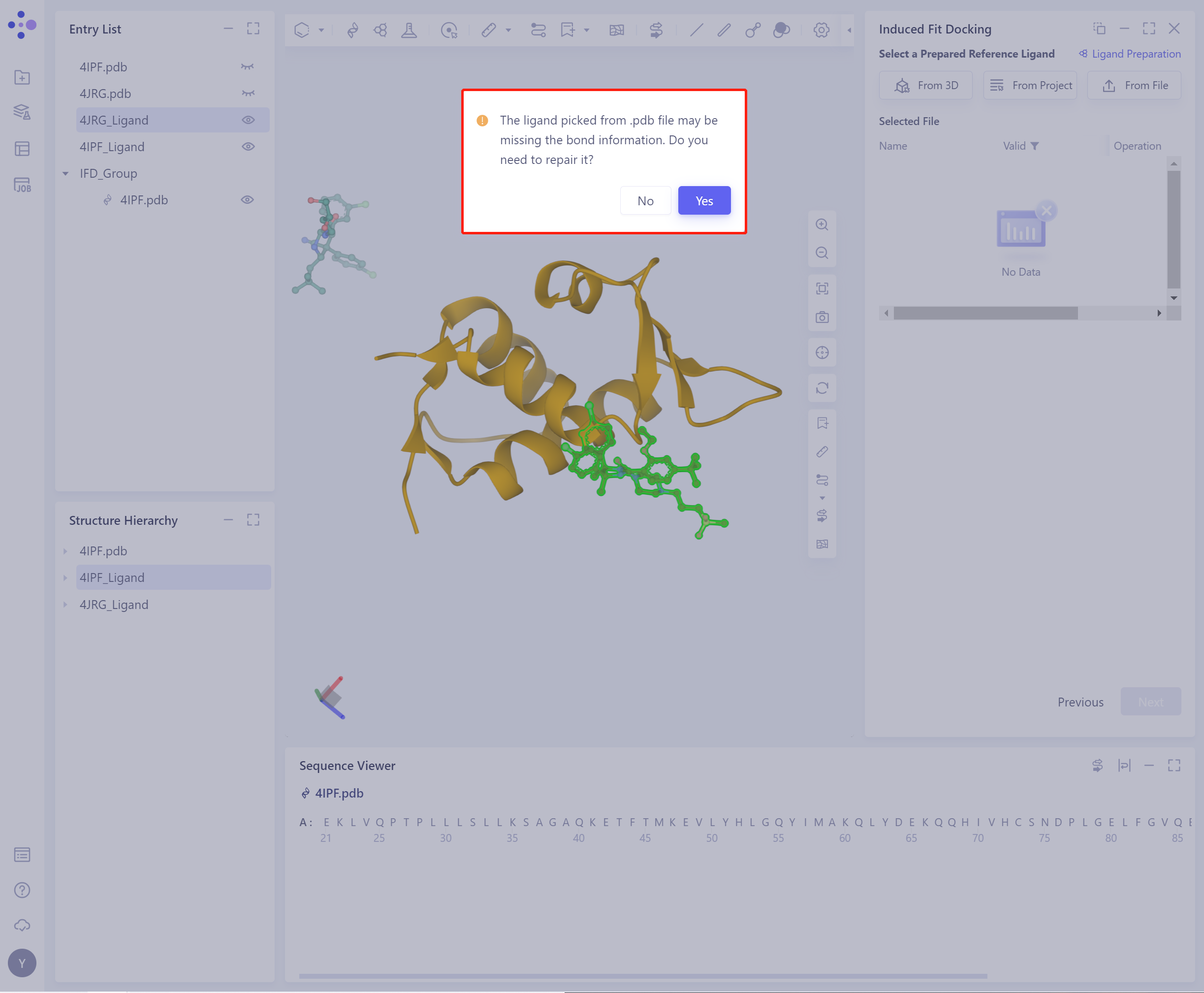
- 选择后的配体会被检查力场,下图为检查中。
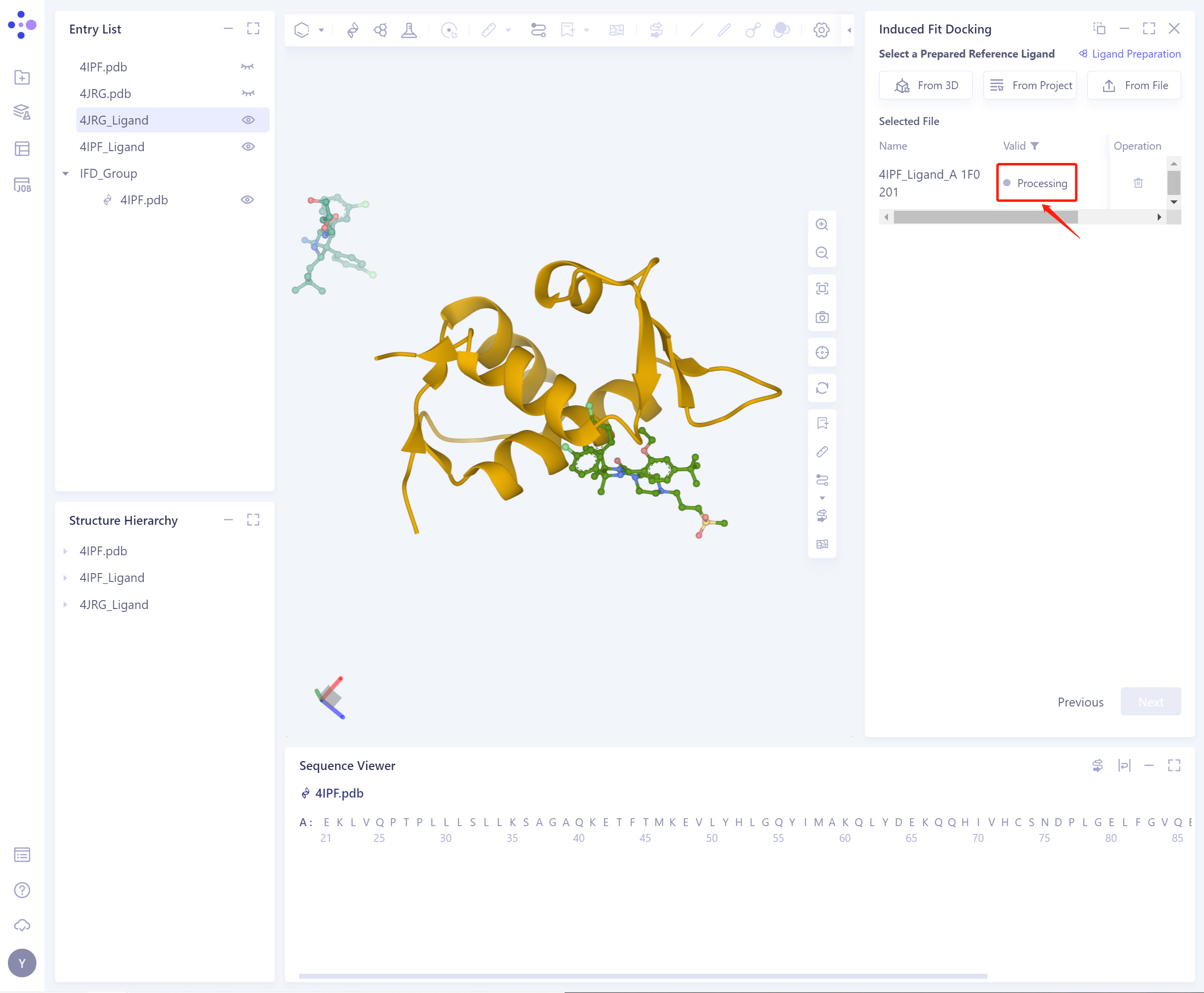
- 若配体力场检查不通过(此处为Valid,即力场检查通过),需要进行配体准备(Ligand Preparation,快捷入口见图中右上红框)。
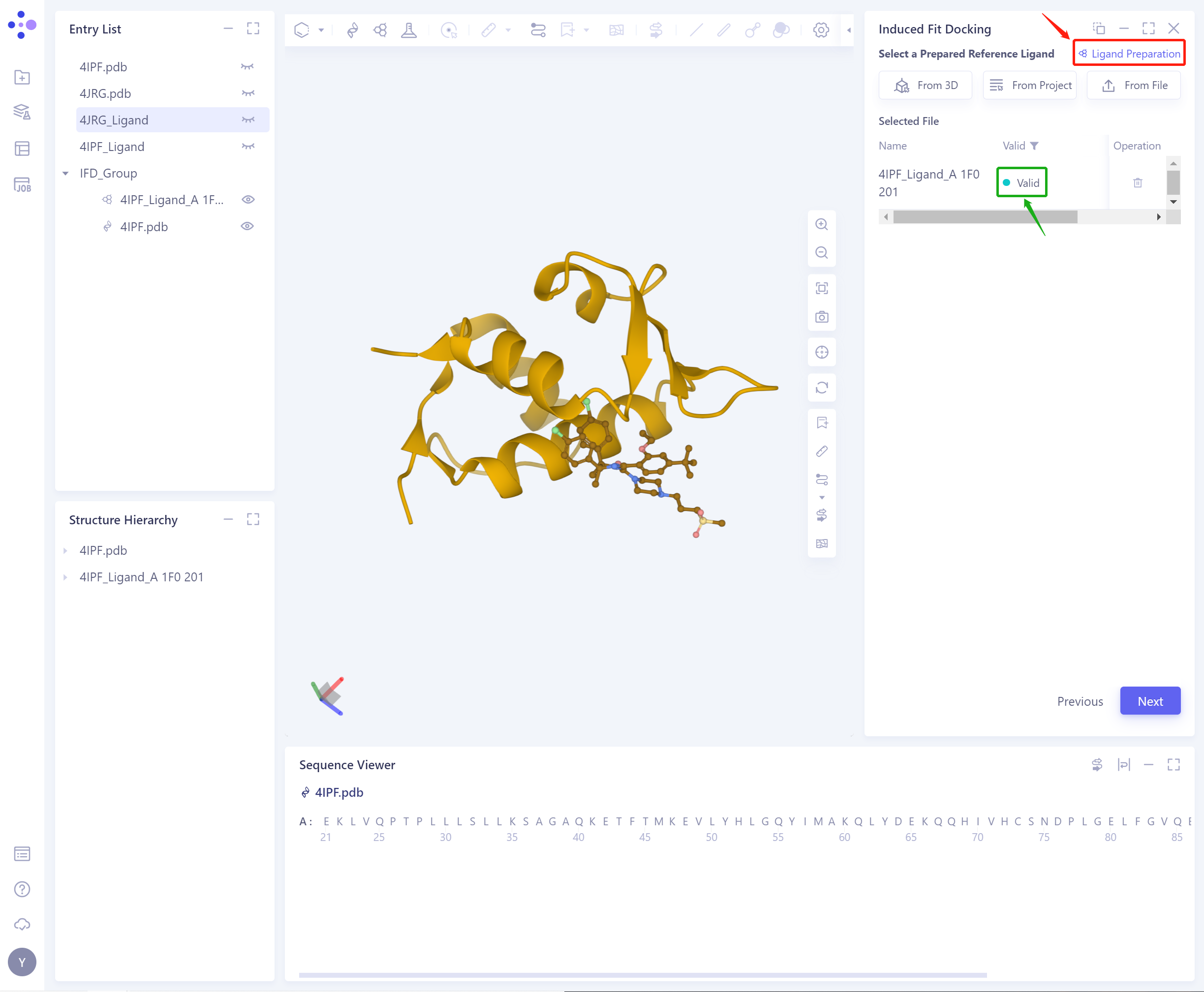
- 配体力场检查通过后,点击Next,可继续使用功能。
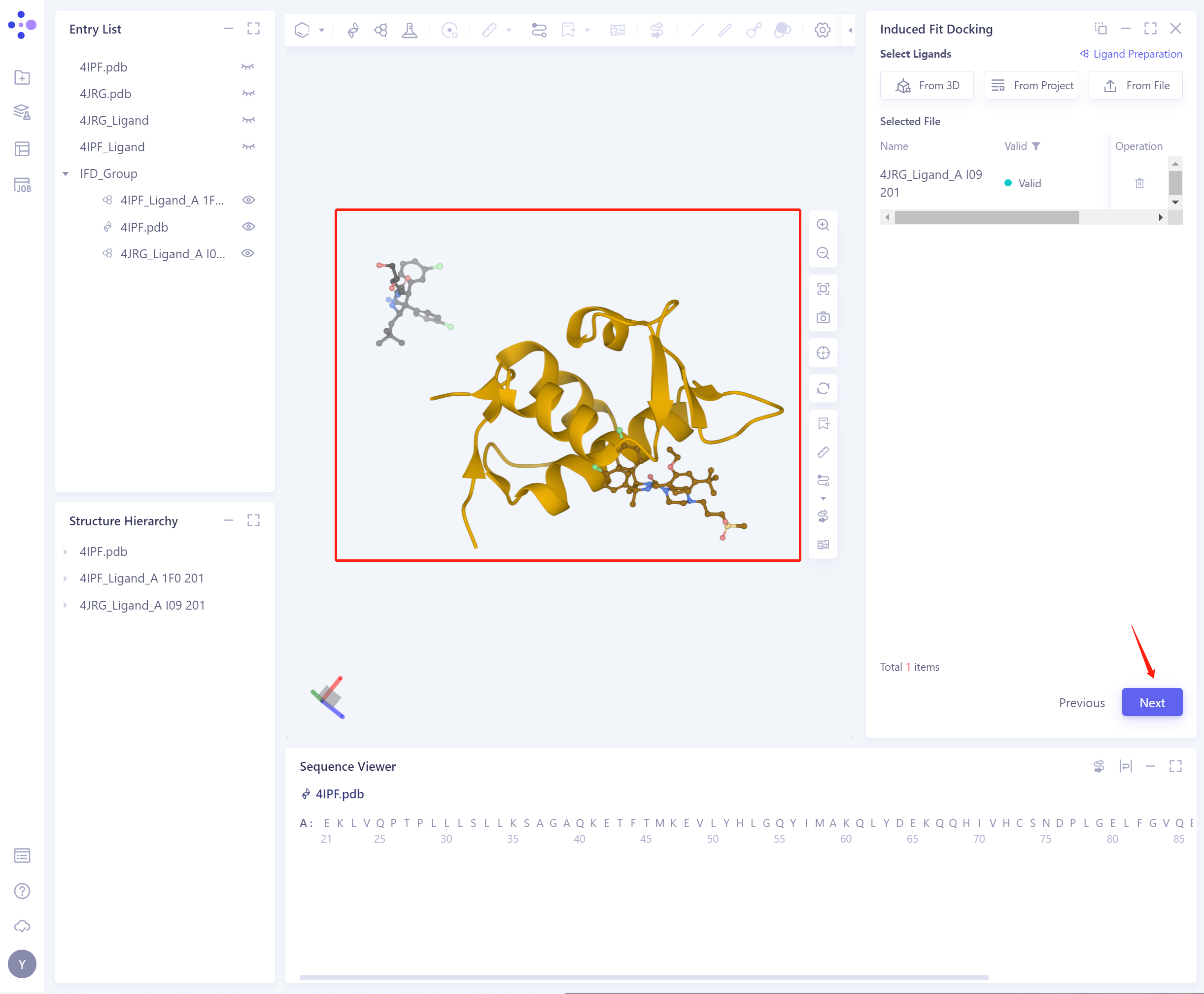
- Select Ligands:(导入ligand有3种方式,同上),导入成功的蛋白和两个配体的结构如图所示,点击Next继续下一步。
-
Pocket Setting:
-
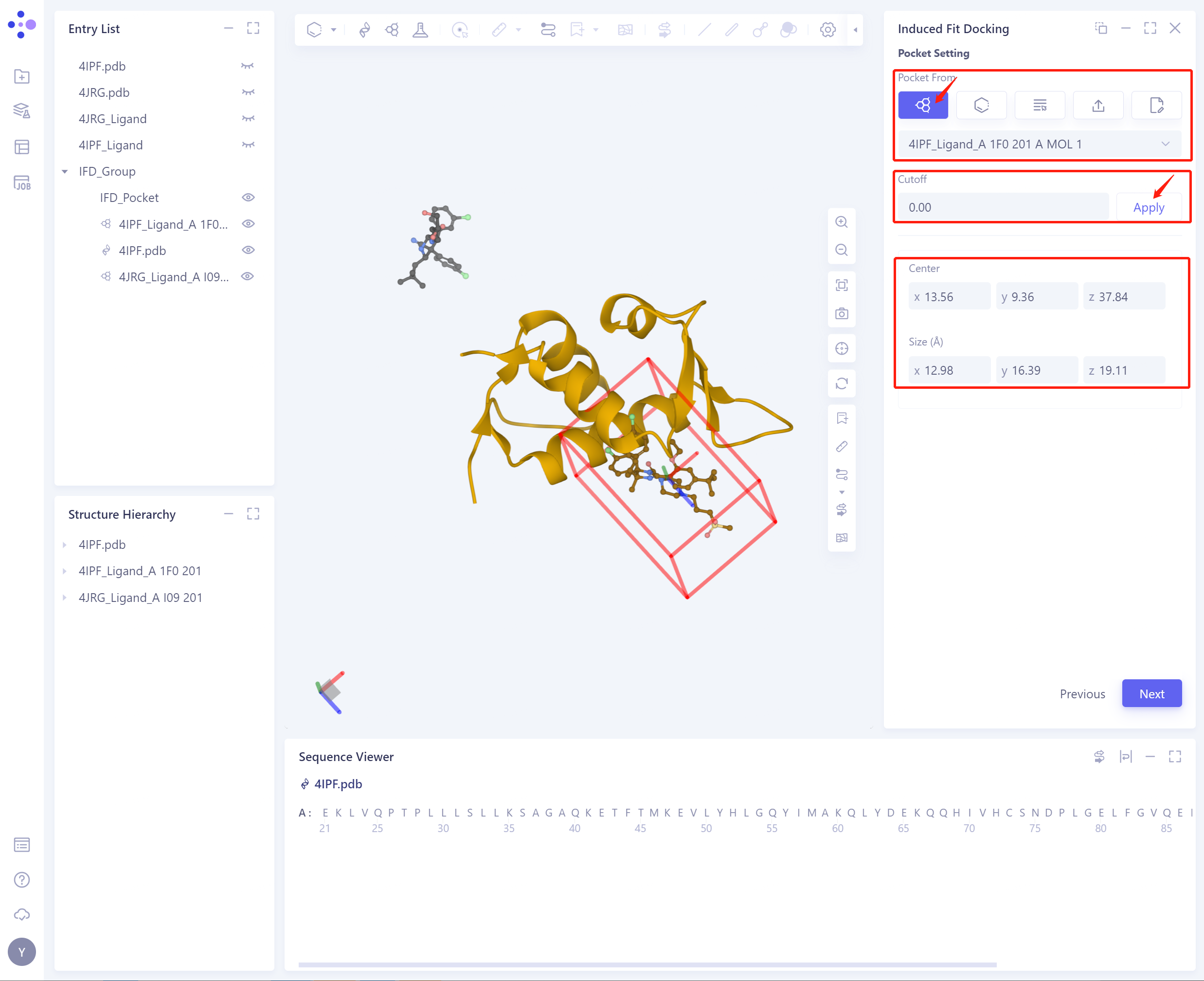
Pocket From:支持5种pocket设置方式:
1)Select Ligand in the structure as center:选择蛋白中的Ligand作为center,确定初始Pocket
-
Cutoff:设置Cutoff值,Pocket的长宽高都会扩大Cutoff的2倍;
-
Center:根据Pocket设置方式,确定Pocket的中心坐标;
-
Size (Å):根据设置的Center和Cutoff,确定Pocket的体积(不得小于1000ų)。
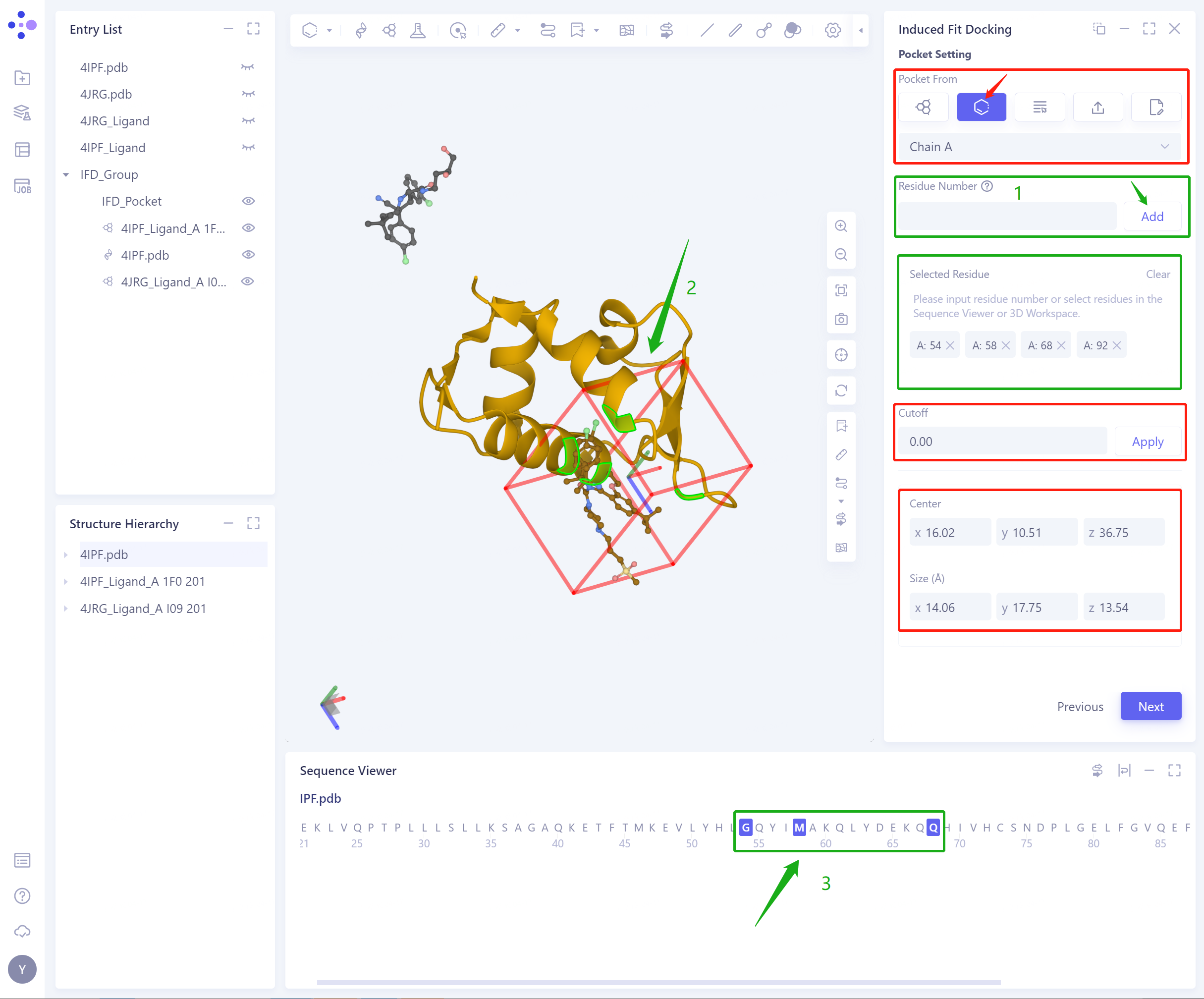
2)Select Residues as Center:选择蛋白残基作为center,确定初始Pocket
-
Residue Number:根据残基序号设置Pocket位置,支持输入Residue Number(1),并在3D workspace(2)和Sequence Viewer(3)中联动选择残基;
-
Cutoff:设置Cutoff值,Pocket的长宽高都会扩大Cutoff的2倍;
-
Center:根据Pocket设置方式,确定Pocket的中心坐标;
-
Size (Å):根据设置的center和cutoff,确定Pocket的体积(不得小于1000ų)。
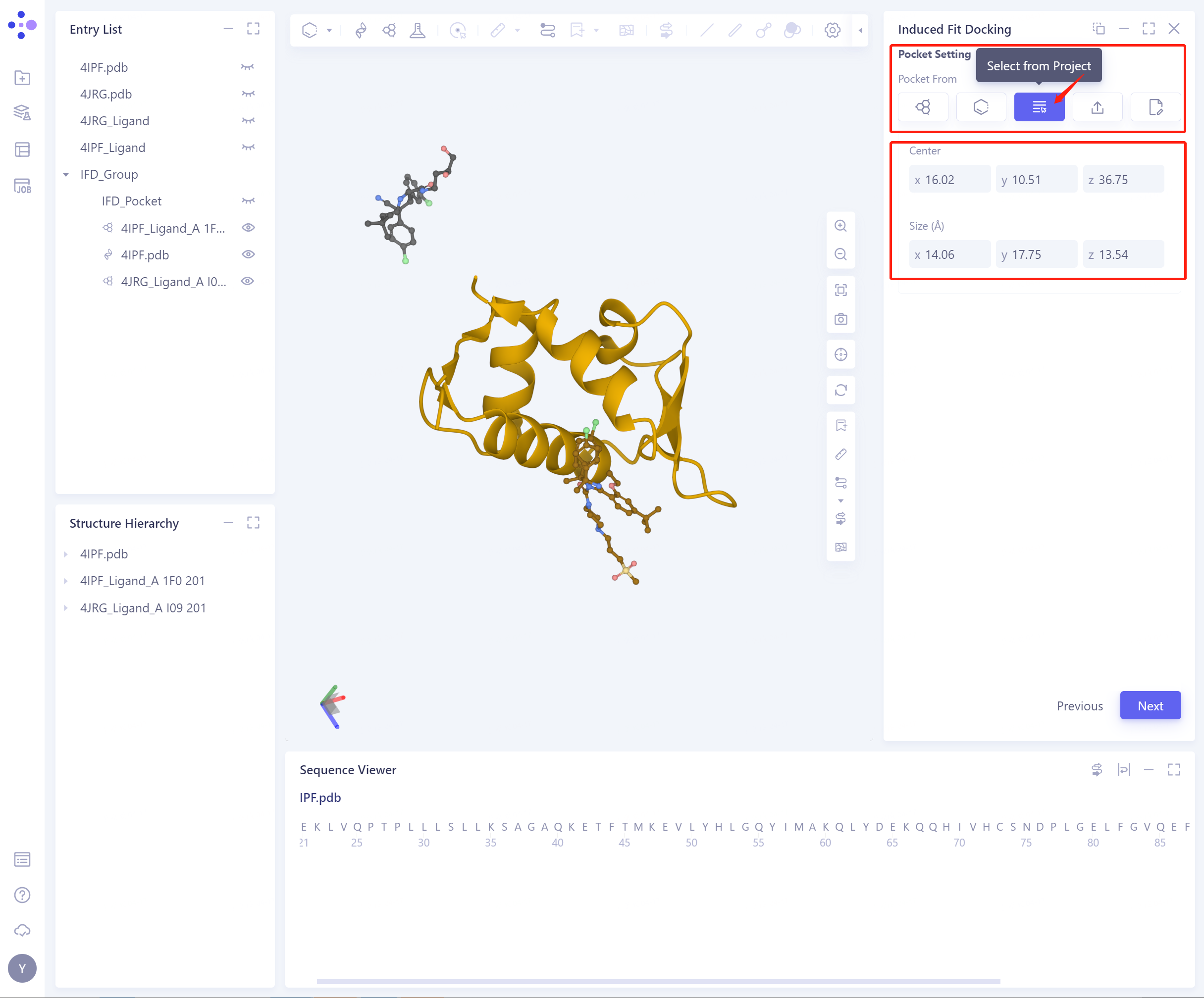
3)Select from project:从project中选择确定初始Pocket
-
Center:支持设置Pocket的中心坐标;
-
Size (Å):支持设置Pocket size,确定Pocket的体积(不得小于1000ų)。
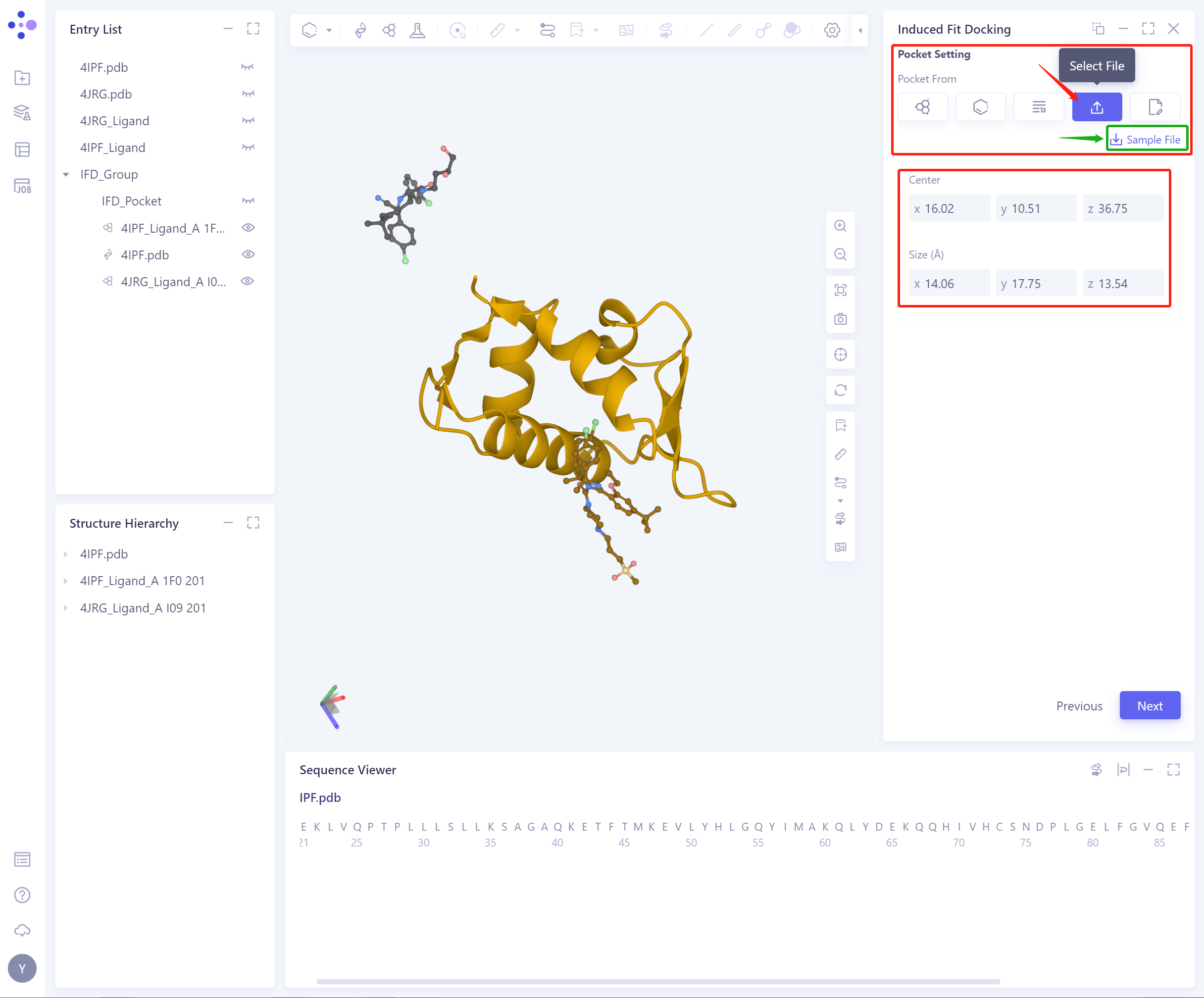
4)Select from File:从File中选择确定初始Pocket(提供pocket设置的Sample File)
-
Center:支持设置Pocket的中心坐标;
-
Size (Å):支持设置pocket size,确定Pocket的体积(不得小于1000ų)。
5)Input:直接手动输入Center坐标、Size大小设置Pocket
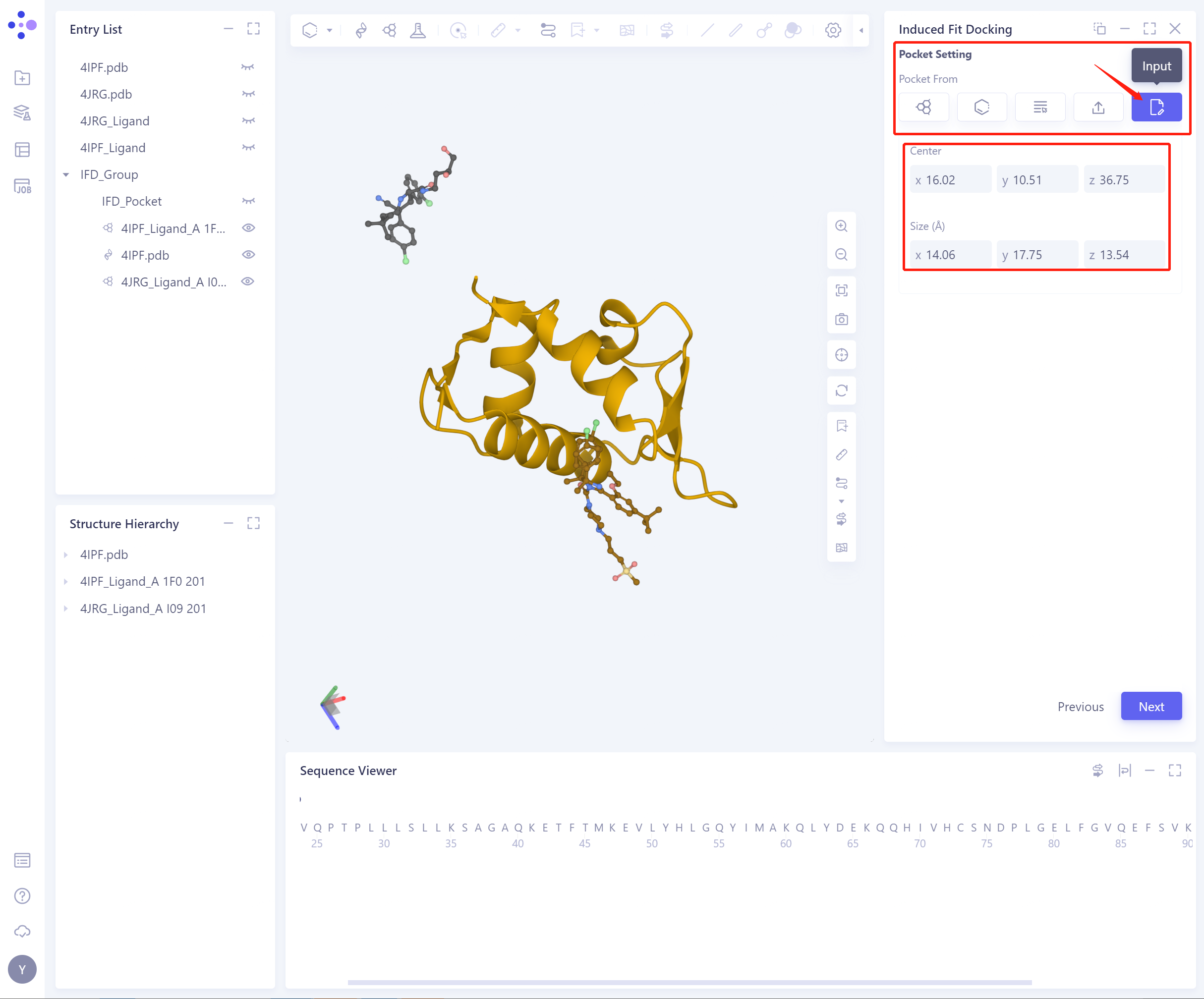
-
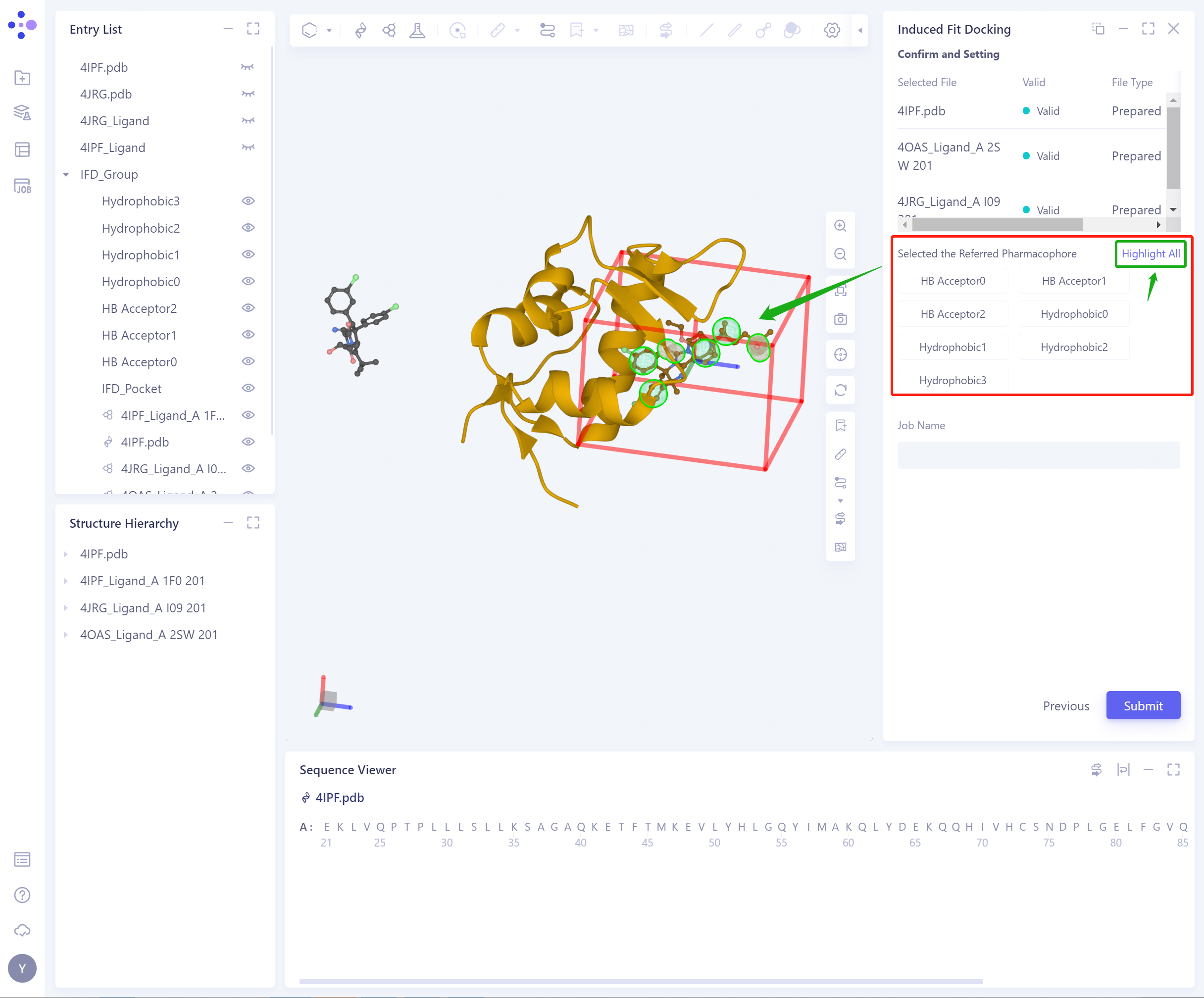
Select Refered Pharmacophore:
- 可以根据Referenece Ligand生成药效团,包含:Hydrophobic、H-Bond Donor、H-Bond Acceptor、Cations、Cation、Anion;
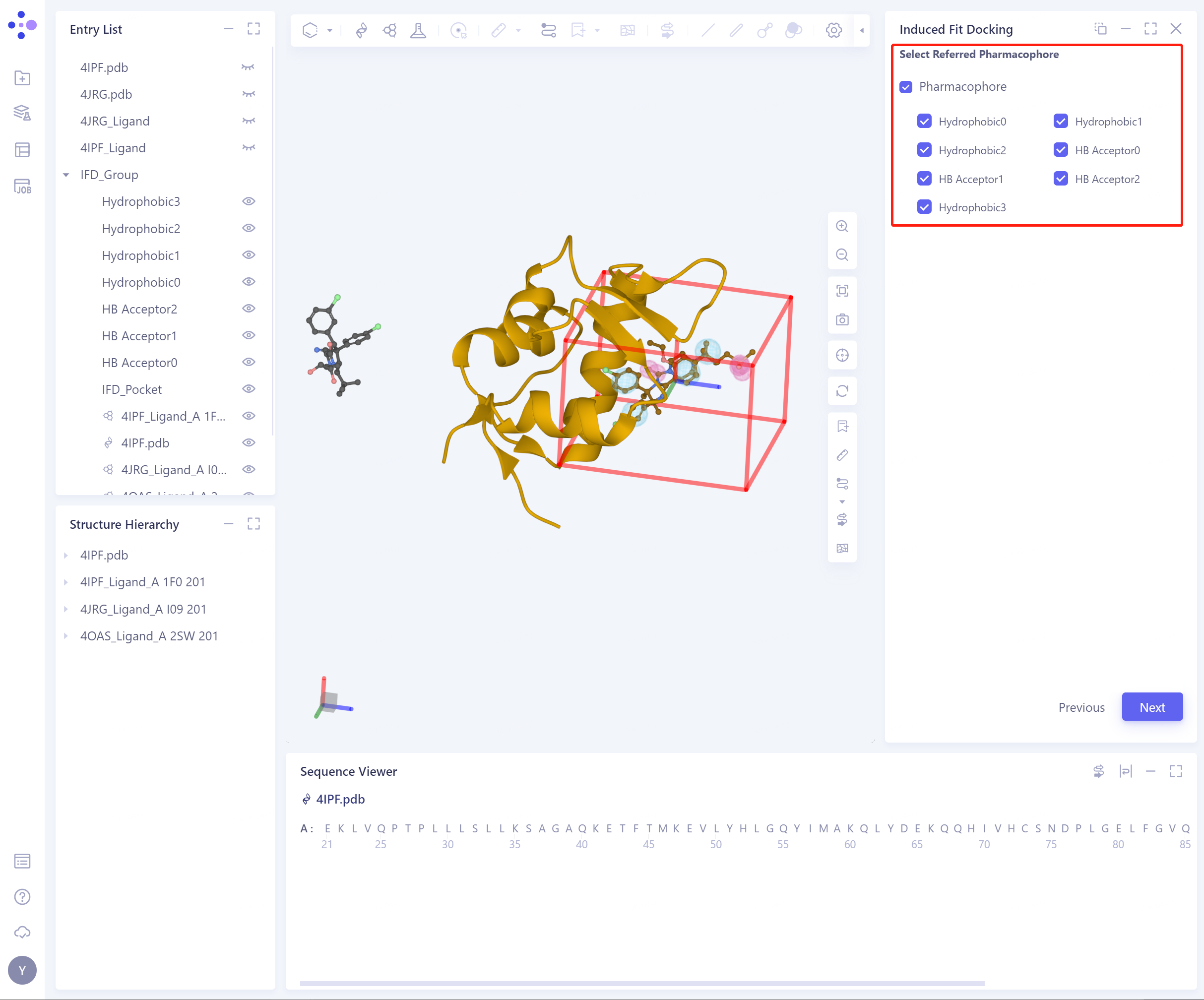
-
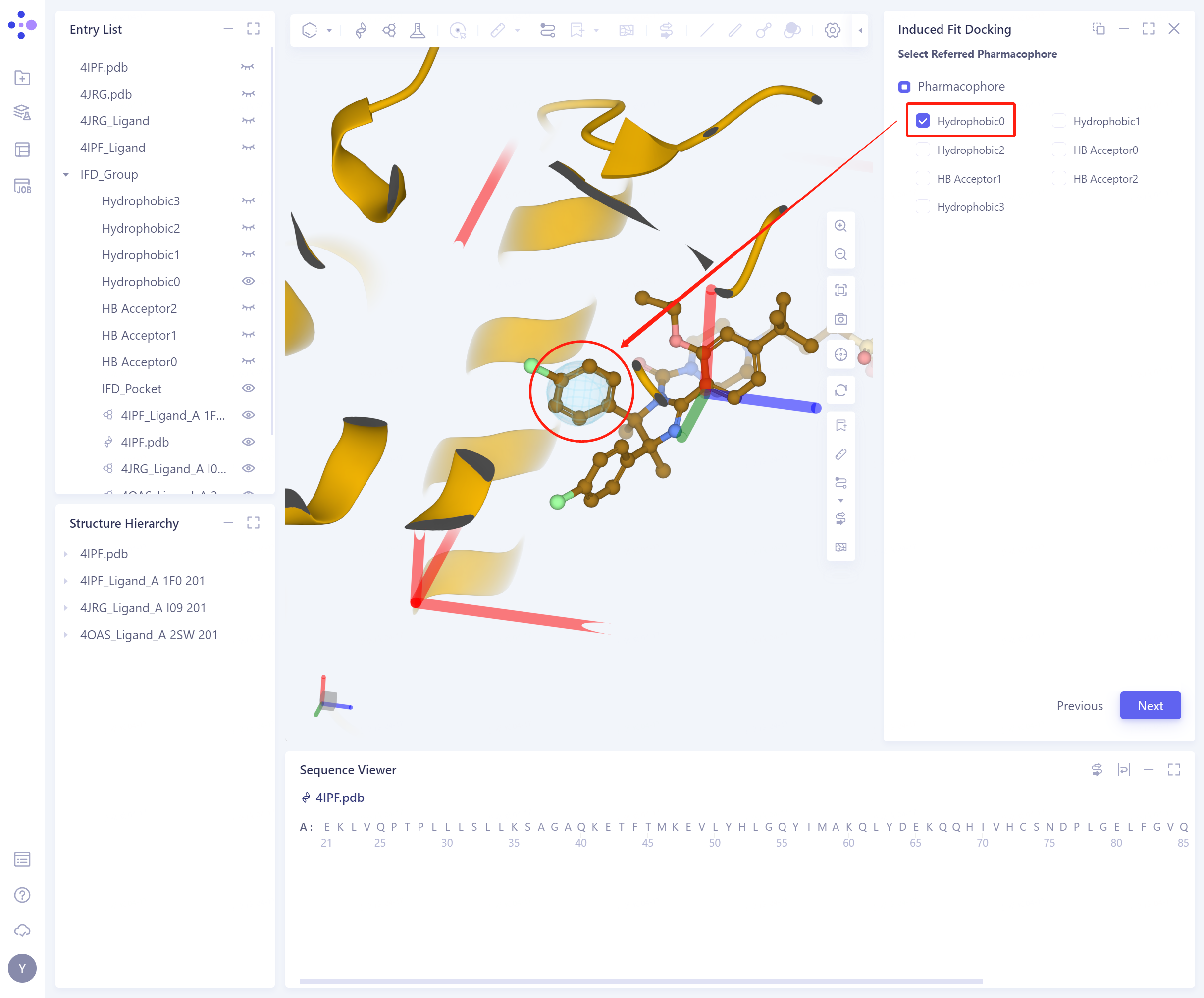
勾选对应的药效团,3D Workspace会自动突显该药效团;
-
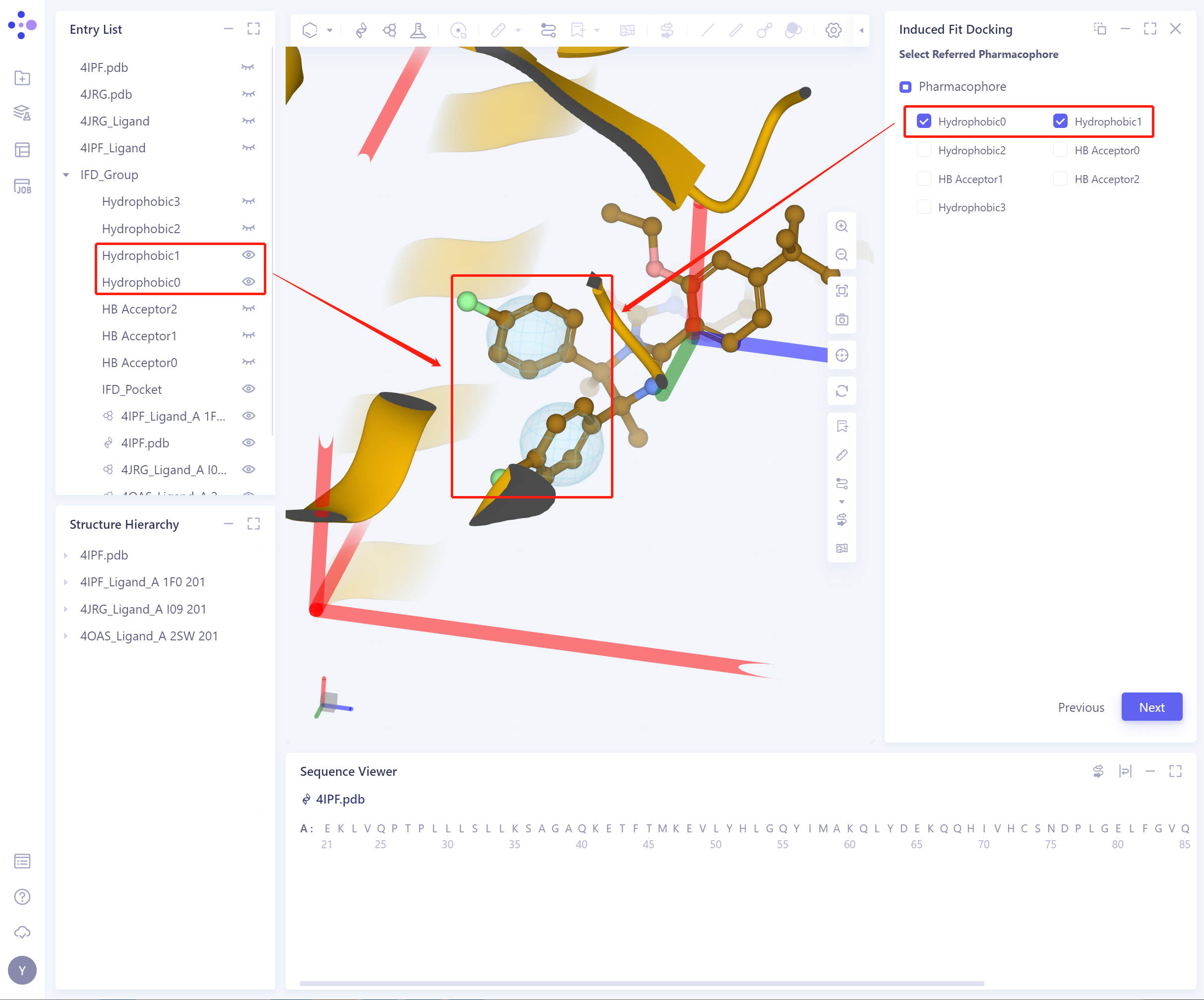
可以根据所选的药效团,确定蛋白的柔性残基。
- 可以在Entry List中直接控制药效团的显隐。
-
Confirm and Setting: 确定输入的蛋白和配体,选中的药效团无误
- 点击Highlight All可以高亮检查选中的药效团。
-
Job Name:对该任务进行命名。
-
Submit:提交任务。
- 路径二:是否选择Reference Ligand: 点击No,不选择Reference Ligands
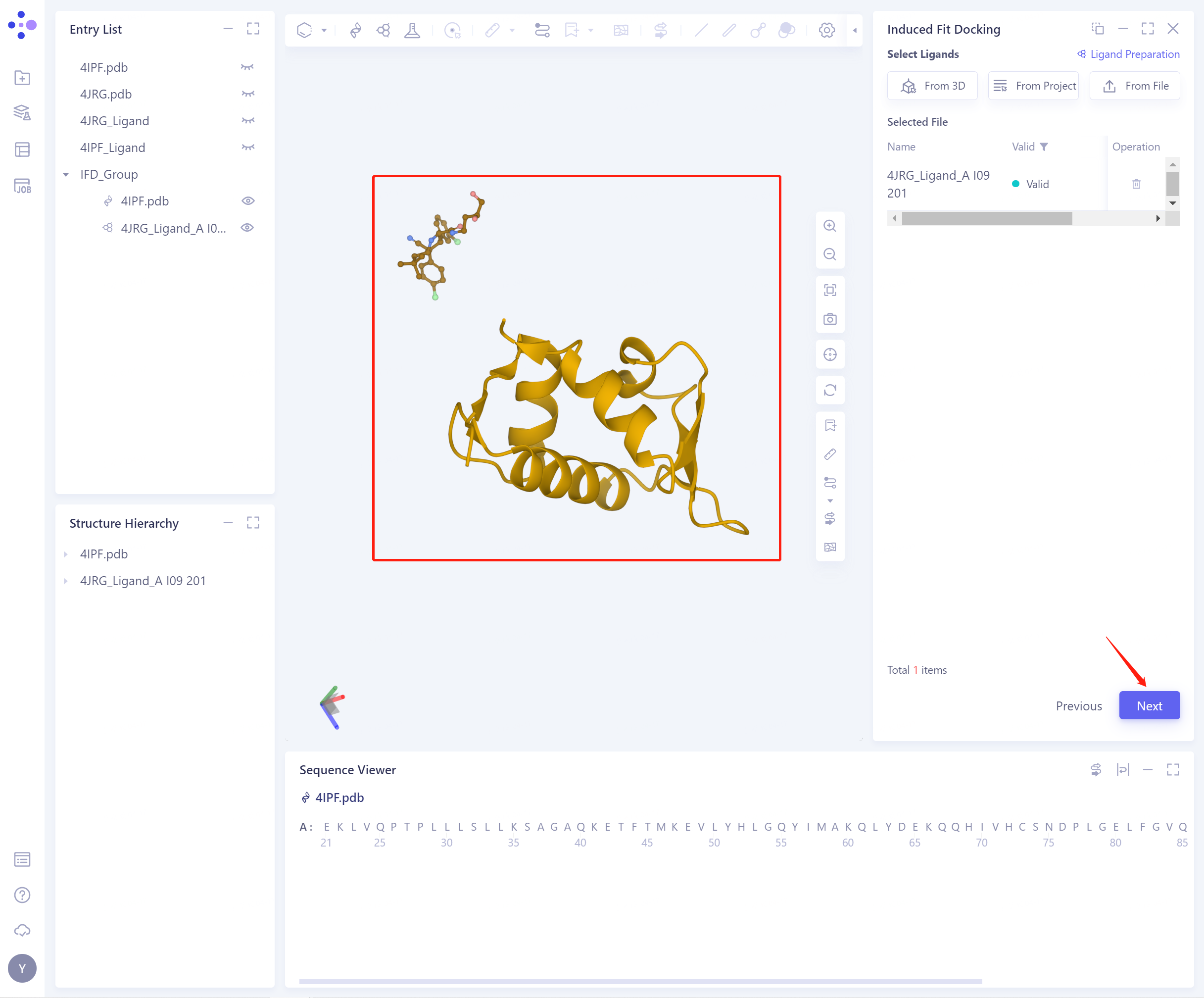
- Select Ligands(导入ligand有3种方式,具体操作同上),导入成功的蛋白和配体的结构如图所示,点击Next进行Pocket Setting。
- Pocket Setting(设置Pocket有5种方式,具体操作同上),设置好的Pocket如图所示:
-
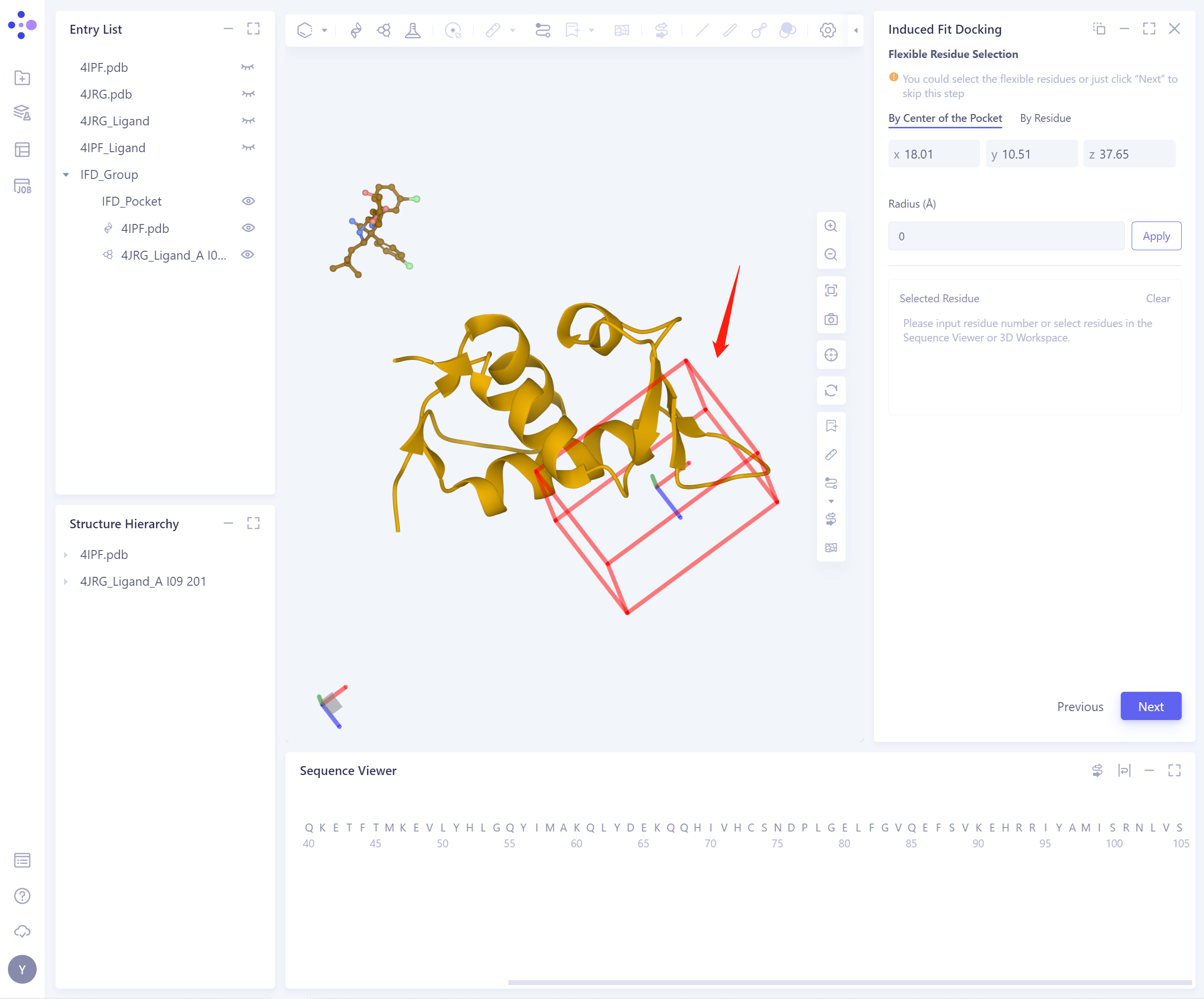
Flexible Residue Selection:
- By Center of the Pocket:根据Pocket中心选择扩展的范围Radius,确定柔性残基(选中的柔性残基会高亮显示);
- By Residue:通过直接选中Residue,确定柔性残基(此时强烈推荐混合使用3D Workspace和Sequence Viewer);
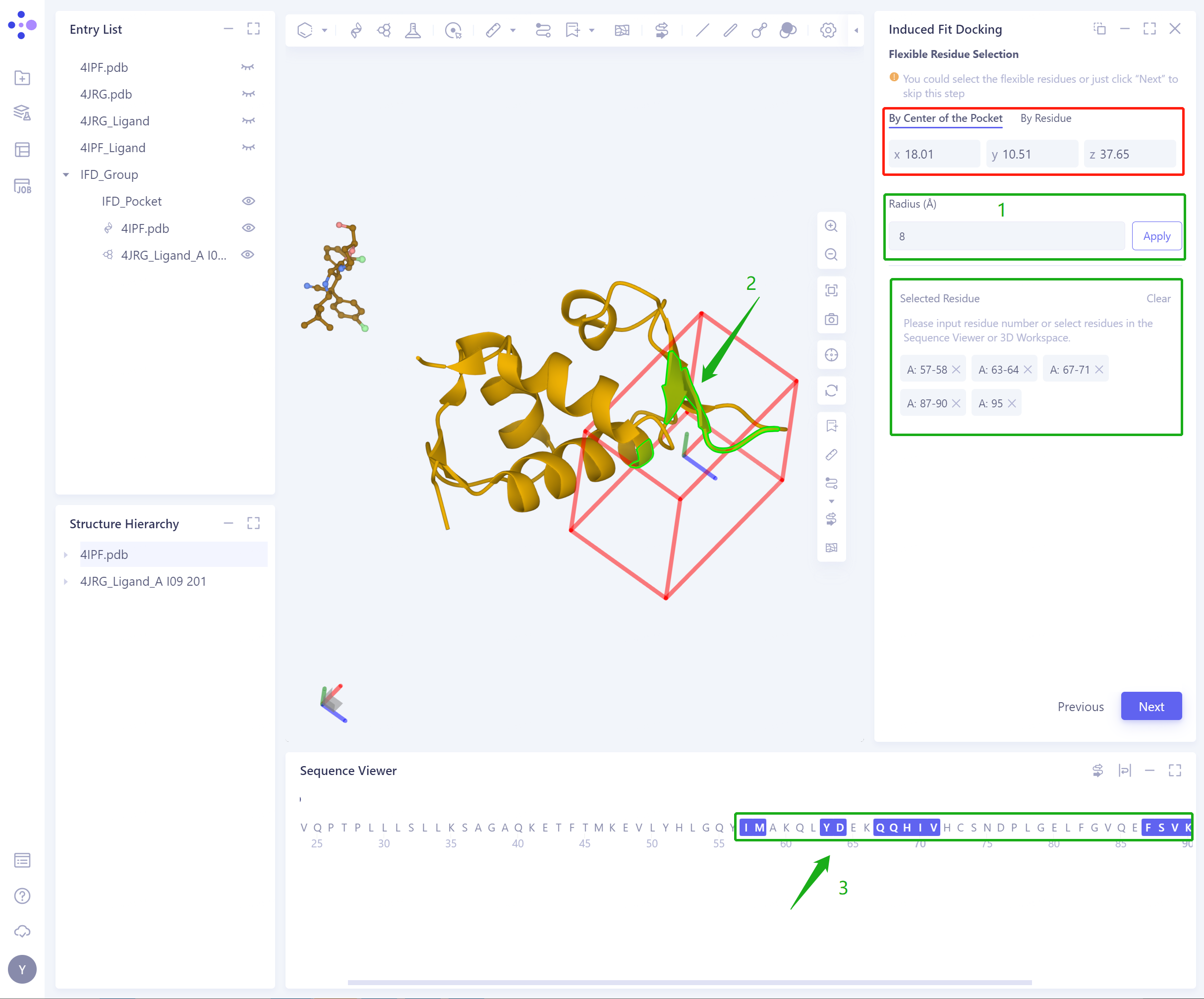
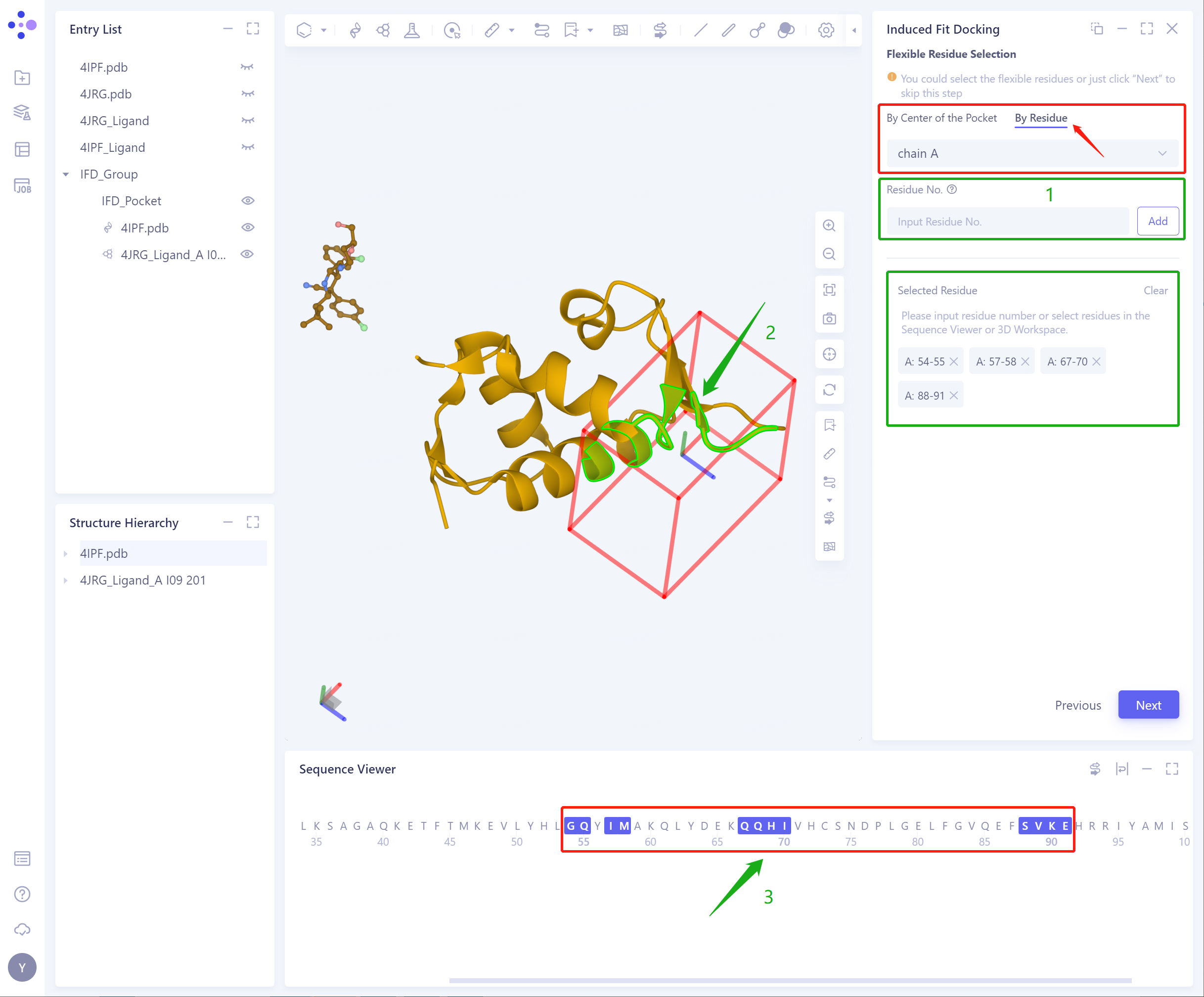
- Confirm and Setting: 确定输入的蛋白和配体,选中的柔性残基无误。
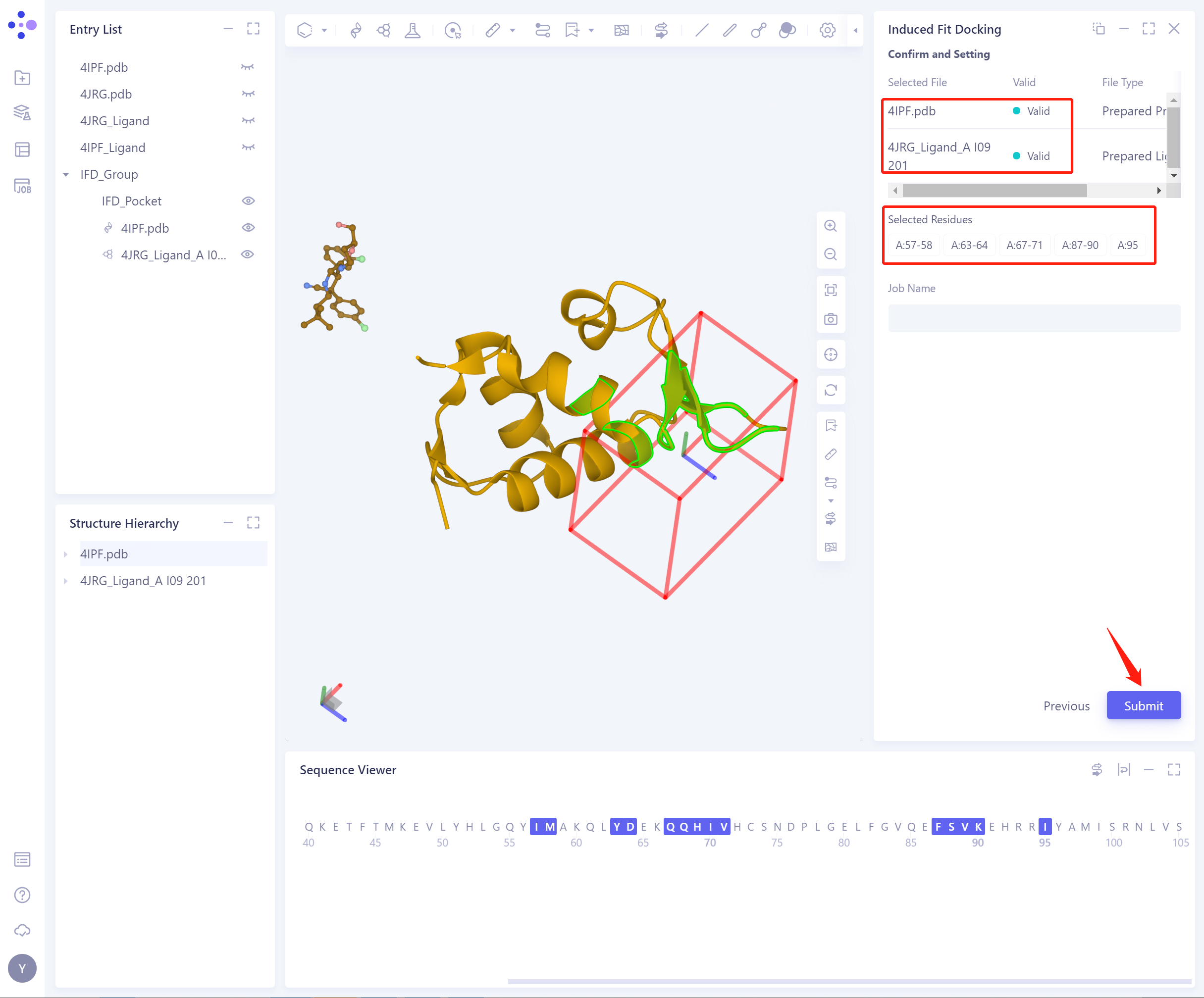
-
Job Name:对该任务进行命名。
-
Submit:提交任务。
3. 结果分析
3.1 入口
-
左侧通用菜单栏Job → 找到该Induced Fit Docking Job。
- 可以通过搜索Job Name找到该任务,也可以通过Job Type的筛选找到。
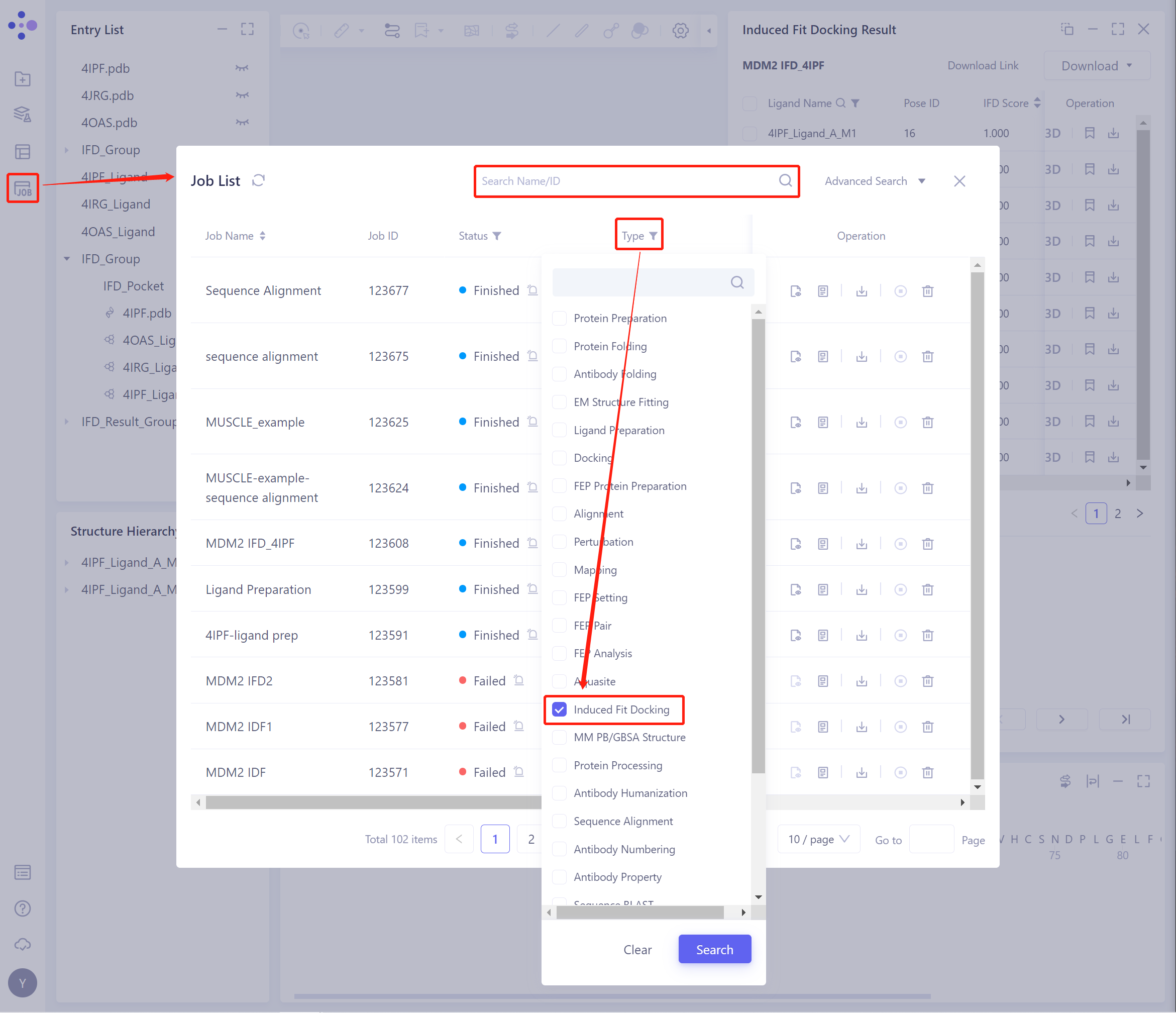
- 选择需要查看的任务,点击Operation列中的Show显示该任务的结果。
3.2 结果展示
-
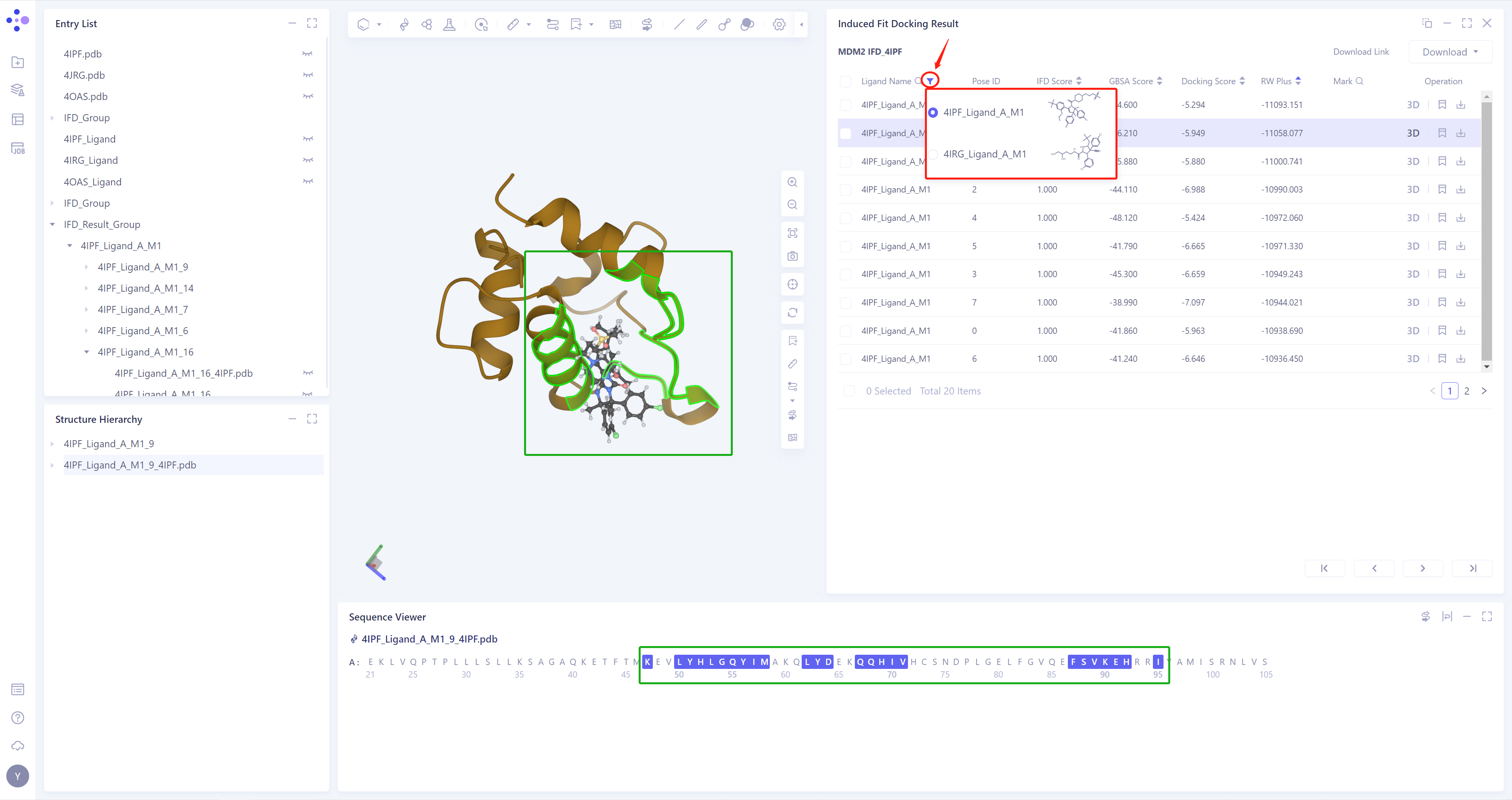
Induced Fit Docking的结果会自动展示在3D Workspace中,并且对应Ligand构象下的柔性残基会高亮显示(Sequence Viewer中联动显示),如图所示;
-
如输入了多个配体,点击红框处按钮可以进行配体结果切换。
-
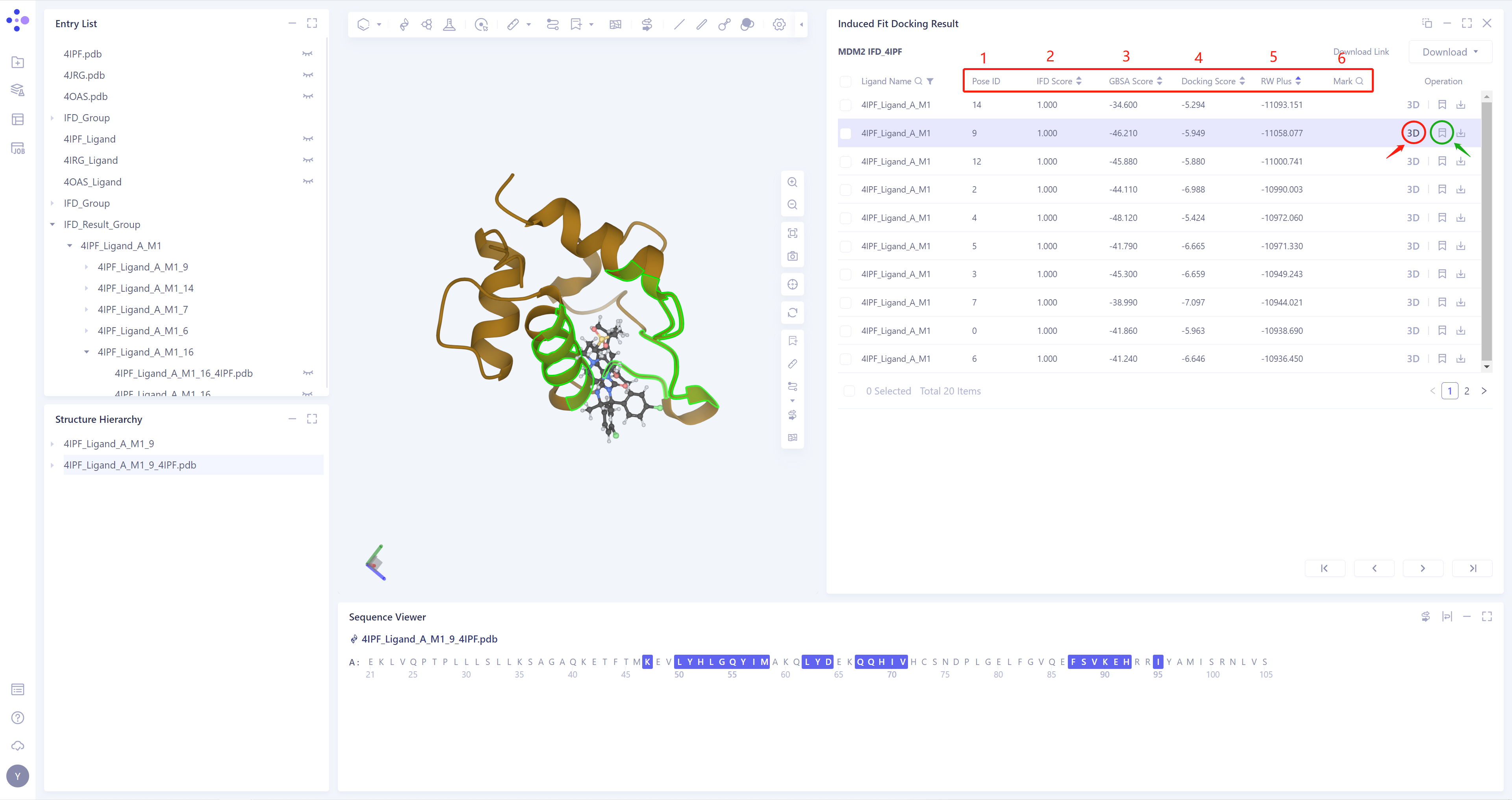
提供5种Docking结果的相关参数:
-
1)Pose ID:根据打分函数(默认为IFD Score),对Docking Pose进行排序;
-
2)IFD Score:根据蛋白和配体的结合模式,给出综合打分(介于0-1之间);
-
3)GBSA Score:根据蛋白和配体的结合模式,GBSA模型给出打分;
-
4)Docking Score:根据蛋白和配体的结合模式,Vina给出的打分;
-
5)RW Plus:RW Plus打分函数(可以处理含有蛋白侧链的打分项);
-
6)Mark:针对部分特殊的数据行,可以点击Mark(绿色框处)进行人工备注,并支持按备注搜索;
-
-
点击Operation列的3D(红色框处),可将对应pose的结果展示在3D workspace中,同时支持键盘↑↓键切换pose(注:该操作根据Pose ID的排序切换);
-
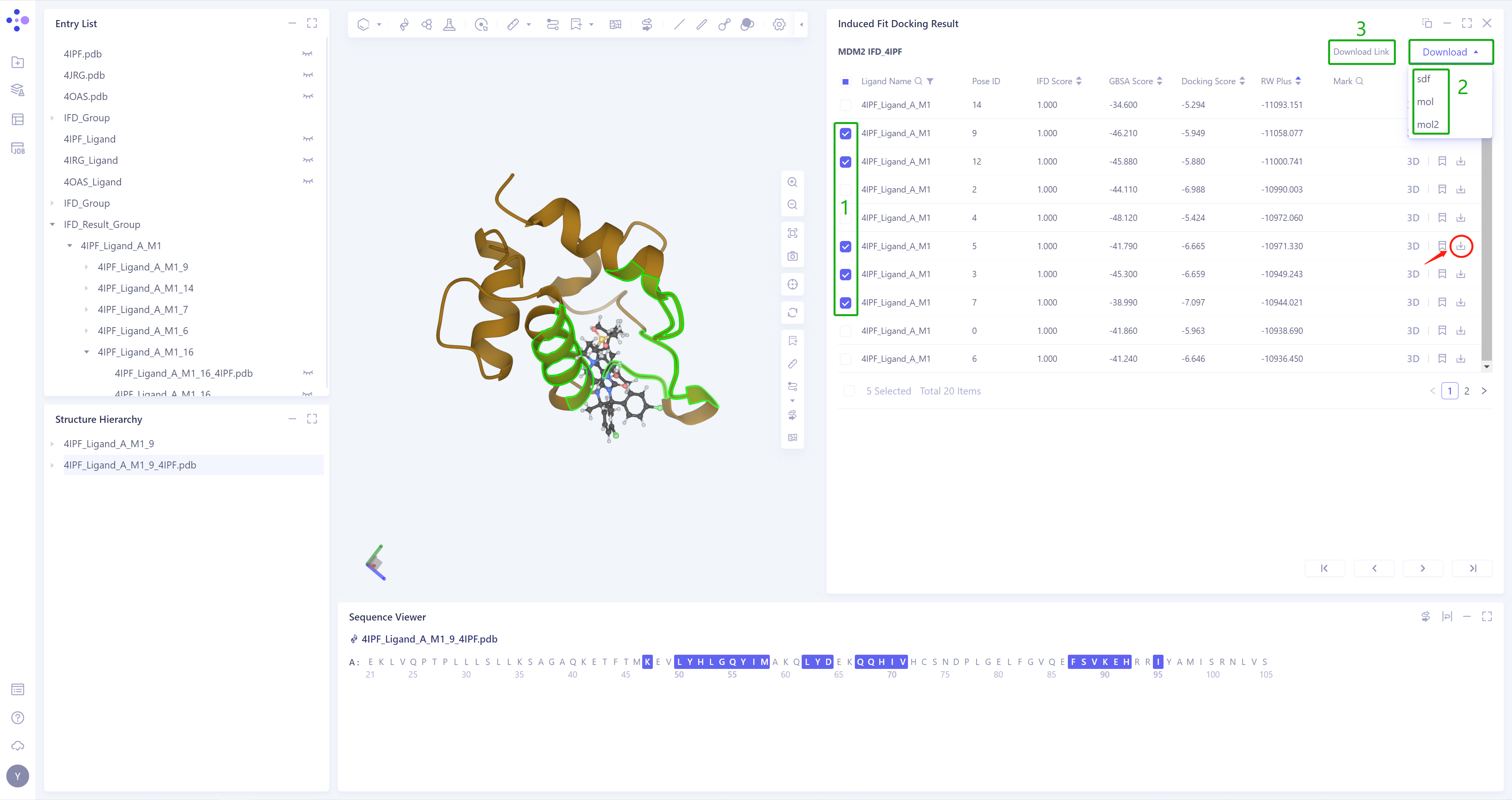
对每个Pose的结果可以下载(红框处),并且支持多Pose结果批量下载;
-
因复选后打包下载的文件较多,可点击Download,再点击Download Link获取下载链接;
-
支持下载.sdf/.mol/.mol2格式文件。